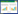文章信息
- 朱平, 陈仁升, 宋耀选, 韩春坛, 刘光琇, 陈拓, 张威
- ZHU Ping, CHEN Rensheng, SONG Yaoxuan, HAN Chuntan, LIU Guangxiu, CHEN Tuo, ZHANG Wei.
- 祁连山中部4种典型植被类型土壤细菌群落结构差异
- Soil bacterial community composition and diversity of four representative vegetation types in the middle section of the Qilian Mountains, China
- 生态学报. 2017, 37(10): 3505-3514
- Acta Ecologica Sinica. 2017, 37(10): 3505-3514
- http://dx.doi.org/10.5846/stxb201602290348
-
文章历史
- 收稿日期: 2016-02-29
- 网络出版日期: 2017-02-17
2. 中国科学院寒区旱区环境与工程研究所, 兰州 730000;
3. 中国科学院大学, 北京 100049
2. Cold and Arid Regions Environmental and Engineering Research Institute, Chinese Academy of Sciences, Lanzhou 730000, China;
3. University of Chinese Academy of Sciences, Beijing 100049, China
土壤微生物参与土壤生态过程, 在生态系统物质循环和能量流动中扮演着重要角色[1-2], 土壤微生物群落多样性是生态系统研究的核心内容之一[3]。长期以来, 土壤微生物研究受技术手段的限制, 无法真实地、更全面地反映土壤微生物群落多样性[4]。新一代高通量测序技术在整体水平上破译了土壤微生物群落结构, 有成本低、通量和覆盖深度高等特点, 将成为研究土壤微生物多样性的常规手段[5]。因此, 采用新一代高通量测序技术, 揭示土壤微生物群落变化规律及其与生境的相互关系, 可为土壤生态系统的优化管理和可持续利用提供理论基础, 具有重要的研究意义[6]。
祁连山为青藏高原东北缘西北―东南走向山系, 位于青藏、蒙新、黄土三大高原交汇地带, 是我国西部生态安全屏障的重要组成部分[7-9]。该地区日照时间长、辐射强、高寒、缺氧等因素相互作用孕育了大量独特的微生物资源[10]。祁连山不同植被的水文响应[11-12]、植被与土壤特性的关系[13-14]、植被群落的演替过程[15-16]的研究较多, 但涉及到祁连山不同植被类型土壤微生物变化特征研究还较少。本研究在祁连山中部选取垫状植被、高寒草甸、沼泽草甸和高寒灌丛4种典型植被类型为研究对象, 采用HiSeq2500高通量测序的方法对其土壤细菌群落结构和多样性进行了研究, 试图回答如下两个问题:(1) 土壤细菌群落结构在4种典型植被类型的差异?(2) 调控4种植被类型土壤细菌群落和多样性的土壤因子是什么?旨在初步揭示祁连山高寒生态系统土壤细菌群落结构和多样性在不同植被类型的差异及变化规律, 为祁连山土壤环境检测、高寒植被恢复和生态环境的可持续发展在微生物层面上提供科学依据。
1 材料与方法 1.1 研究区概况研究区位于青藏高原东北缘祁连山中部托勒南山葫芦沟流域内(38°12′—38°17N, 99°50′—99°54E, 阴坡), 垂直景观梯度分异明显[17]。多年平均温度为-3.1—3.6℃, 年平均降水为430—650 mm, 属大陆性高寒山区气候[18]。研究区内主要的土壤类型为高山草甸土、高山灌丛草甸土、沼泽土和寒漠土。该地区仅有冷暖两季, 冷季漫长, 暖季较短, 植被生长期短, 生物生产力低。植被类型随海拔由高到低依次为垫状植被带(3900—4200 m)、高山草甸带(3700—3900 m)、沼泽草甸带(3500—3700 m)、亚高山灌丛草甸带(3200—3500 m), 研究区3500—3700 m由于该海拔范围内地势较为平坦, 雨水在此汇集, 排水不畅形成沼泽草甸。垫状植被带(cushion plants, CP)优势种为囊种草(Thylacospermum caespitosum)、垫状点地梅(Androsace tapete)和水母雪莲(Saussurea medusa);高寒草甸带(alpine meadow, AM)优势种为小嵩草(Kobresia pygmaea)、矮嵩草(K. humilis)和藏嵩草(K. tibetica);沼泽草甸带(SM)优势种为藏嵩草(K. tibetica)、矮嵩草(K. humilis)和线叶嵩草(K. capillifolia), 伴生种为早熟禾(Poa annua)和垂穗披碱草(Elymus nutans);高寒灌丛带(alpine shrub, AS)优势种为金露梅(Potentilla fruticosa)和高山柳(Salix cupularis)。
1.2 样地设置和取样方法研究区内选择上述4种不同海拔高度的植被群落为实验样地, 样地概况参见朱平论文[19]。在大概1000 m海拔梯度范围内, 每隔大约300 m设置一个样地, 每个样地分别设置3个20 m×20 m样方为重复, 每个样方间隔约100 m, 在每个样方内用直径4.5 cm土钻S型采集5个表层20 cm深度的土样, 混合后约500 g分别装入自封袋并做标记。土样挑除石块、根系等杂物并保存在4 ℃的冰盒, 带回实验室后立即用新鲜土壤测定土壤微生物生物量碳和氮, 然后将土样分两份:其中1份土样风干用于土壤理化性质分析;另1份土样实验室冰箱-20 ℃保存用于土壤DNA提取。采样时间为2013年7月。
1.3 测定方法 1.3.1 土壤主要理化性质和土壤微生物生物量碳、氮的测定土壤pH采用电位法测定, 水土比为2.5:1;土壤含水量(soil moisture, SM)采用烘干法测定, 将盛有新鲜土样的铝盒, 置于105 ℃的恒温干燥箱烘6—8 h, 烘至恒重;土壤有机碳(SOC)采用重铬酸钾氧化外加热法;总氮(TN)采用半微量凯氏法;总磷(TP)采用酸溶—钼锑抗比色法, 称取风干土样, 加高氯酸和氢氟酸加热, 土壤中含磷矿物及有机磷化合物全部转化为正磷酸盐进入溶液, 然后用钼锑抗比色法测定[20]。土壤微生物生物量碳、氮(microbial biomass carbon, MBC;microbial biomass nitrogen, MBN)采用氯仿熏蒸培养法测定[21-22]。
1.3.2 土壤DNA提取和测序采用PowerSoil DNA提取试剂盒(MoBio Inc., USA), 称取0.3—0.5 g土壤样品, 按试剂盒规定的实验步骤提取土壤总DNA。利用引物515F(GTGCCAGCMGCCGCGGTAA)与806R(GGACTACHVGGGTWTCTAAT)扩增其V4区基因片段。修饰后的引物含有不同的Barcode以区分不同样品。PCR反应体系为50 μL, 其中含ddH2O23 μL, Premix Taq DNA聚合酶25 μL, DNA模板量1 μL(5—10 ng), 正向引物0.5 μL(20 ng/μL), 正向引物0.5 μL(20 ng/μL)。PCR扩增反应条件为:95 ℃, 5 min;30×(94 ℃, 45 s;56 ℃, 45 s;72 ℃, 45 s);72 ℃, 10 min。每个样品重复扩增3次。PCR扩增以后, 三管同一样品合并, 用GeneJET试剂盒(Thermo Scientific Inc., USA)纯化, 用NanoDrop 2000(Thermo Scientific Inc., USA)测定PCR产物浓度, 样品送至北京诺禾致源测序公司(Novegene, China)进行高通量测序。
1.3.3 生物信息分析及数据处理根据Barcode序列拆分各样品数据, 然后截取Barcode和引物的序列使用FLASH[23]对进行拼接;高通量序列数据使用QIIME[24]进行数据处理:利用UPARSE[25]软件对全部有效序列进行聚类, 默认以97%序列相似度对序列聚类获得OTUs(operational taxonomic units, 操作分类单元);从每个OTUs选取一个代表性序列, 以Greengenes数据库[26]为参考, 使用RDP Classifier[27]对OUT进行物种注释, 置信水平为80%;最后对样品数据均一化处理, 以样品中数量最少的为标准, 统一抽取45160条有效序列来研究细菌群落结构。通过计算物种丰富度(OTUs)和系统发育多样性Faith′s PD指数[28](Faith′s Phylogenetic diversity)来表示土壤细菌群落的α多样性。
1.4 数据分析所有数据均为平均值±标准误, 采用SPSS 11.5和R软件的数据包VEGAN进行数据统计分析。采用单因素方差比较不同植被土壤理化性质、优势细菌菌群和土壤细菌α多样性指数的差异性。Pearson系数分析土壤因子和土壤细菌多样性指数的相关性。利用R软件的VEGAN数据包进行微生物群落结构的Mantel和CCA分析;显著性水平设定为α=0.05。相关图的制作在Origin 8.0中完成。
2 结果与分析 2.1 土壤理化性质研究区4种植被类型土壤pH在6—7之间, 曾微酸性, 土壤pH变异幅度较窄。沼泽草甸长期处于积水状态, 土壤含水量较高, 植物有机残体残留在土壤中, 厌氧的土壤环境抑制了好氧微生物的代谢活动, 土壤有机碳不能完全分解, 积累在土壤表层, 沼泽草甸土壤有机碳含量高于其它植被类型。垫状植被土壤总氮显著低于其它3种植被类型(P < 0.05), 主要由于垫状植被地表凋落物较少, 草本覆盖度低, 土壤养分积累量低于其它3种植被类型(表 1)。
| 样地 Sampling site |
pH | 土壤含水量 Soil moisture |
土壤有机碳 Soil organic carbon/ (g/kg) |
总氮 Total nitrogen/ (g/kg) |
总磷 Total phosphorus/ (g/kg) |
碳氮比 Ratio of carbon: nitrogen |
| CP | 6.97±0.10a | 0.11±0.01a | 21.07±3.48a | 4.09±1.02a | 0.66±0.24a | 5.46±1.01a |
| AM | 6.30±0.19bc | 0.29±0.01b | 76.92±4.11bc | 7.10±0.77b | 0.81±0.08a | 11.25±1.94b |
| SM | 6.13±0.06c | 0.60±0.01c | 77.13±0.73c | 7.67±0.14b | 0.68±0.01a | 10.07±0.28ab |
| AS | 6.53±0.06b | 0.33±0.01d | 57.85±10.95b | 7.04±0.18b | 0.67±0.03a | 8.31±1.78ab |
| CP:垫状植被cushion plants;AM:高寒草甸alpine meadow;SM:沼泽草甸swamp meadow;AS:高寒灌丛alpine shrub; 同行不同小写字母表示不同植被类型间存在差异(P < 0.05) | ||||||
如图 1所示, 在研究区4种植被类型土壤微生物生物量碳的大小顺序为:沼泽草甸>高寒草甸>高寒灌丛>垫状植被。沼泽草甸的平均微生物生物量碳为1537.7 mg/kg, 分别为高寒草甸、高寒灌丛和垫状植被的2.23、4.45倍和6.48倍。沼泽草甸的平均微生物生物量碳含量显著大于高寒草甸、高寒灌丛和垫状植被(P < 0.05);高寒草甸的平均微生物生物量碳含量显著大于高寒灌丛和垫状植被(P < 0.05);高寒灌丛和垫状植被的平均土壤微生物生物量碳含量差异不显著(P>0.05)。研究区4种植被类型土壤微生物生物量氮与土壤微生物生物量碳的变化规律基本一致。
|
| 图 1 土壤微生物生物量碳氮 Fig. 1 Soil microbial biomass carbon and nitrogen of four representative vegetation types CP:垫状植被cushion plants;AM:高寒草甸alpine meadow;SM:沼泽草甸swamp meadow;AS:高寒灌丛alpine shrub;不同小写字母表示不同植被类型间存在差异(P < 0.05) |
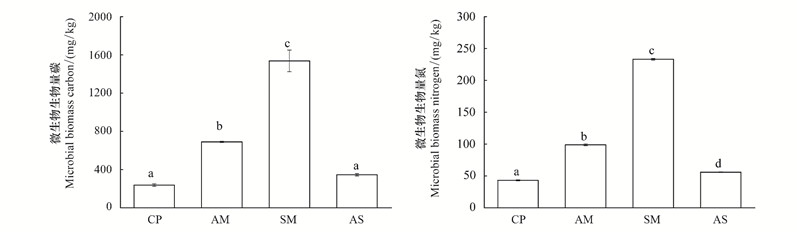
高通量测序结果显示所有样品一共获得713386条有效序列, 其中最少序列为54161条, 最多序列为67678条(平均序列条数是59449条)。这些序列的99.1%可以分类到不同的细菌门类, 0.9%与数据库比对分类到古菌门类。图 2可以看出祁连山中部4种典型植被类型土壤细菌优势门类为放线菌门(Actinobacteria)(23.10%), 酸杆菌门(Acidobacteria)(18.90%)、α-变形菌门(Alphaproteobacteria)(10.59%)、厚壁菌门(Firmicutes)(8.13%)和芽单胞菌门(Gemmatimonadetes)(6.12%), 它们的平均相对丰度大于5%, 占了总序列的63%以上;而γ-变形菌门(Gammaproteobacteria)、绿弯菌门(Chloroflexi)、疣微菌门(Verrucomicrobia)、β-变形菌门(Betaproteobacteria)、拟杆菌门(Bacteroidetes)、δ-变形菌门(Deltaproteobacteria)、浮霉菌门(Planctomycetes)、硝化螺旋菌门(Nitrospirae)的平均相对丰度大于1%但低于5%。此外还发现了相对丰度小于1%的其它41个稀有门类, 它们占到总序列的不到5.4%。
|
| 图 2 土壤细菌优势门类的相对丰度 Fig. 2 The relative abundance of dominant bacterial phylum in soil separated according to four representative vegetation types |
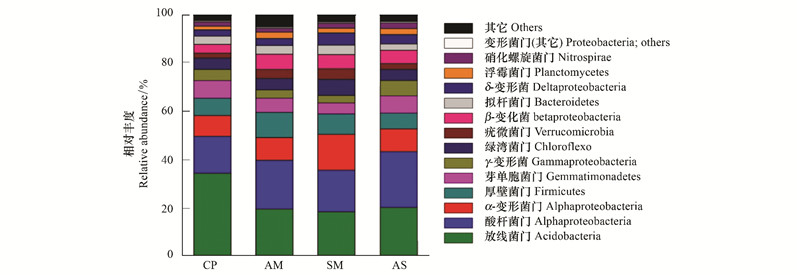
本研究通过测序了解了祁连山中部4种典型植被类型土壤细菌的优势菌群, 并对相对丰度大于5%的细菌门类进行分析, 图 3可以看出垫状植被土壤中放线菌门的相对丰度显著高于其他3种植被类型(P < 0.05);而沼泽草甸土壤中α-变形菌门的相对丰度显著高于其它3种植被类型(P < 0.05), 芽单胞菌门的相对丰度显著低于其它3种植被类型(P < 0.05)。
|
| 图 3 5个土壤优势细菌菌群相对丰度的差异 Fig. 3 The relative abundance of five soil dominant bacterial phylum of four representative vegetation types |
土壤可以提供细菌群落生长繁殖的微环境, 而不同的植被类型通过改变土壤的微环境间接影响了土壤细菌群落结构的组成。土壤理化性质和细菌群落结构的相关性采用Mantel检验方法(Mantel tests)分析, 从表 2可以看出土壤细菌群落结构与土壤pH、土壤含水量、土壤有机碳和总氮呈现显著相关(P < 0.05)。
| 变量Variables | r | P |
| pH | 0.600 | 0.001 |
| 土壤有机碳Soil organic carbon | 0.412 | 0.007 |
| 总磷Total phosphorus | 0.154 | 0.143 |
| 土壤含水量Soil moisture | 0.572 | 0.001 |
| 总氮Total nitrogen | 0.285 | 0.017 |
| 碳氮比Ratio of carbon: nitrogen | 0.091 | 0.250 |
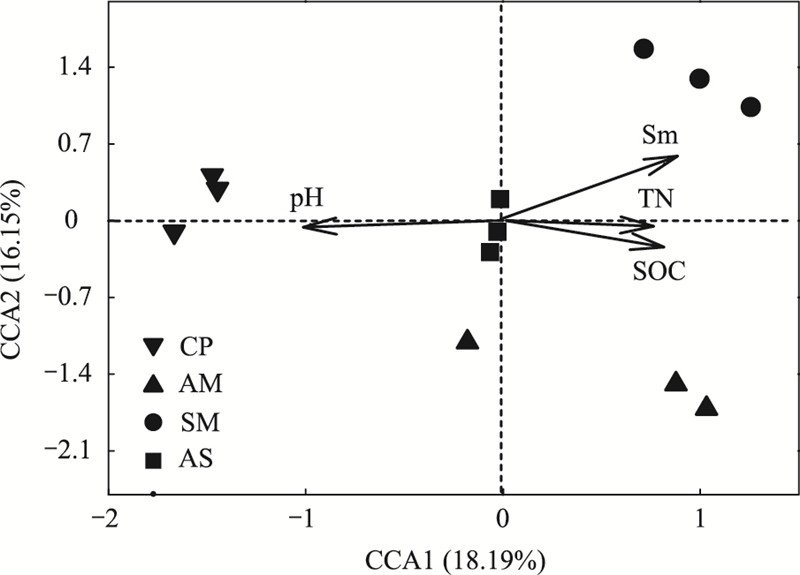
利用R语言bioENV筛选出最能体现土壤细菌群落结构变化的4个土壤因子, 研究结果与Mantel tests方法一致, 将经过筛选的土壤理化因子与细菌群落结构进行典范对应分析(canonical correspondence analysis, 图 4), CCA二维排序图可以直观地给出研究对象与环境变量之间的关系, 排序轴与箭头连线夹角表示环境因子与排序轴的相关性, 夹角越小表明关系越密切, 而箭头连线表示环境因子与研究对象相关程度的大小, 连线越短, 相关性越小, 反之越大[29]。蒙特卡罗检验(Monte Carlo test)发现, 第一轴与全部轴均呈极显著差异(P < 0.01), 故CCA分析排序结果可信。在土壤pH、含水量、有机碳和总氮中, 土壤pH和含水量对表层土壤细菌群落结构具有较大影响(P=0.001和P=0.003)。同时不同植被类型土壤细菌群落发生明显分异, 垫状植被土壤细菌群落主要处于土壤pH较高区域, 而沼泽草甸土壤细菌群落主要聚类于土壤含水量较高的区域, 4种植被群落土壤细菌群落结构较为分散。
|
| 图 4 土壤细菌群落结构与理化性质的CCA分析 Fig. 4 Canonical correspondence analysis (CCA) of the soil bacterial communities and associated soil properties Sm:土壤含水量Soil moisture;SOC:土壤有机碳Soil organic carbon;TN:总氮Total nitrogen |
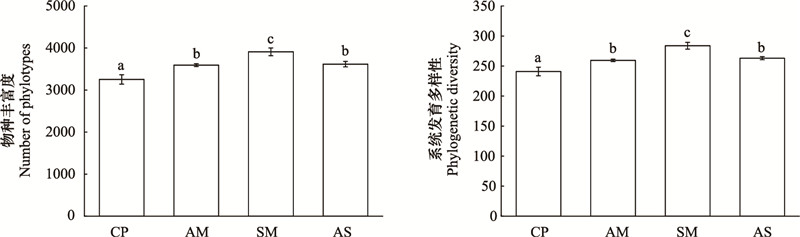
由图 5可知, 4种植被类型土壤细菌物种丰富度变化范围为(3253±112)—(3910±92), 系统发育多样性变化范围为(240.9±7.1)—(283.8±5.7)。垫状植被土壤细菌物种丰富度和系统发育多样性值最低, 而沼泽草甸土壤细菌物种丰富度和系统发育多样性值最高。沼泽草甸土壤细菌物种丰富度和系统发育多样性显著高于其它3种植被类型(P < 0.05);而垫状植被土壤细菌物种丰富度和系统发育多样性显著低于其它3种植被类型(P < 0.05)。为探讨土壤细菌α多样性与土壤因子的关系, 对土壤细菌α多样性(物种丰富度和系统发育多样性)与土壤pH、含水量、有机碳等6个土壤因子做相关性分析。表 3表明土壤含水量、土壤有机碳和总氮与细菌物种丰富度和系统发育多样性有极强的相关性(P < 0.01)。土壤pH与细菌物种丰富度和系统发育多样性负相关, 其相关系数分别为-0.688和-0.676。其它土壤因子与细菌物种丰富度和系统发育多样性未达显著性水平(P>0.05)。
|
| 图 5 4种植被类型土壤细菌物种丰富度和系统发育多样性指数 Fig. 5 Soil bacterial OTUs phylotypes richness and phylogenetic diversity of four representative vegetation types |
| 变量 Variables |
物种丰富度 OTUs |
系统发育多样性 Phylogenetic diversity |
| pH | -0.688* | -0.676* |
| 土壤有机碳Soil organic carbon | 0.773** | 0.721** |
| 总磷Total phosphorus | 0.157 | 0.135 |
| 土壤含水量Soil moisture | 0.875** | 0.900** |
| 总氮Total nitrogen | 0.804** | 0.786** |
| 碳氮比Ratio of carbon: nitrogen | 0.447 | 0.387 |
| **P < 0.01;*P < 0.05 | ||
祁连山高寒生态系统是全球变化的敏感区域, 其微生物组成和功能影响生态系统转化的方向和进程[10]。土壤微生物生物量虽然约占不到土壤有机质的5%, 却是植物可利用养分的重要来源, 能灵敏的反映环境因子的变化[30-31]。沼泽草甸平均微生物生物量碳氮大于高寒草甸、高寒灌丛和垫状植被。这可能与沼泽草甸土壤水分含量较高有关, 而土壤水分是调节高寒草甸生态系统土壤微生物物质转化的关键因子[32]。同时土壤微生物量碳又与土壤有机质密切相关[33], 本研究中, 土壤有机碳含量的大小排列顺序为沼泽草甸>高寒草甸>高寒灌丛>垫状植被, 与土壤微生物生物量碳氮排序一致。王启兰等[32]对藏嵩草草甸、小嵩草草甸、矮嵩草草甸、禾草草甸、杂类草草甸及金露梅灌丛土壤微生物数量和生物量研究发现沼泽化藏嵩草草甸表层土壤细菌数量和微生物生物量碳最高, 与本研究结果基本一致。这说明不同植物群落归还土壤植物残体数量和质量的不同, 可能是造成土壤微生物生物量碳氮差异的主要原因[34]。
土壤细菌是土壤微生物的重要组成部分, 绝大多数土壤优势细菌种类基本相同, 主要包括10个左右的细菌类群[35-36]。Chu等[37]在青藏高原西北部研究表层土壤细菌群落结构发现放线菌门、α-变形菌门、酸杆菌门、绿弯菌门和芽单胞菌门5大门类为研究区的优势类群。厚壁菌门、γ-变形菌门、β-变形菌门、δ-变形菌门、拟杆菌门、浮霉菌门6大门类为平均相对丰度小于5%大于1%的细菌门类, 与本研究基本一致。而Yuan等[38]在念青唐古拉南面沿海拔梯度取样研究高山草原土壤细菌群落发现酸杆菌门、变形菌门、芽单胞菌门为研究范围内最主要的3个细菌门类。Zhang等[39]在青藏高原北麓河流域分析草甸、草原和荒漠草原土壤细菌群落结构差异发现主要优势菌群为变形菌门、放线菌门、酸杆菌门、拟杆菌门4个门类。这可能当地的气候、水文、土壤、植被条件不同有关, 似乎没有两种土壤包含完全一致的微生物群落结构。研究区4种植被土壤细菌优势菌群, 与其它研究相比厚壁菌门相对丰度较高, 这可能与厚壁菌门更能适应祁连山干冷的土壤环境和利用有限的土壤养分有关[40]。芽单胞菌门在沼泽草甸相当丰度显著低于垫状植被和高寒灌丛, DeBruyn等[41]发现芽单胞菌门更适合在土壤含水量较低的环境下生存。垫状植被土壤放线菌门相对丰度显著高于其它3个植被类型, 放线菌最适生长环境土壤pH值偏碱性, 而垫状植被土壤pH相对其它3种植被类型更高些而含水量又低于其它3种植被类型, 土壤环境更适宜放线菌的生长。
研究区4种植被类型土壤细菌群落结构和α多样性与土壤pH、土壤含水量、土壤有机碳和全氮显著相关(P < 0.05)。土壤pH是影响土壤细菌群落分布最主要影响因子。Rousk等[42]对具有pH梯度的农田土壤180m距离(小尺度)内土壤微生物群落结构和多样性采用454高通量测序分析, 结果表明土壤细菌群落结构组成和多样性与土壤pH密切相关。Fierer等[43]利用末端限制性片段长度多态性分析了美洲大陆从北到南土壤细菌群落多样性和生物地理分布模式, 发现土壤细菌群落丰富度和多样性与土壤pH相关。Lauber等[44]对其研究进行补充, 利用454高通测序发现土壤pH是土壤细菌群落空间变异的驱动因素。Shen等[45]在长白山研究6种典型植被类型, 采用高通量技术研究土壤细菌群落组成和多样性随海拔的分布规律, 发现土壤pH是驱动土壤细菌分布的影响因子, 与本研究结论一致。同时土壤含水量、有机碳和全氮也是土壤细菌群落结构和多样性的主要影响因子。Zhang等[39]采用高通量测序分析发现土壤含水量和碳氮比是影响土壤细菌群落结构的主要因素。Shen等[46]在高寒苔原小尺度海拔梯度研究发现土壤碳和氮是影响土壤细菌海拔梯度分布的关键环境因素, 并强调土壤含水量与土壤细菌丰富度和多样性密切相关。而Chu等[37]在对青藏高原西北部大尺度研究表层和亚表层土壤细菌群落分布时发现总碳和碳氮比是青藏高原微生物生物地理分布的主要影响因子。植被类型可能通过凋落物和根际分泌物影响了土壤微环境间接地改变了土壤细菌的群落结构和多样性。高寒草甸具有密实的根系, 土壤有机碳含量较高;而垫状植被草本覆盖度低, 土壤有机碳和总氮含量低, 土壤微环境的营养差异可能改变本研究区4种植被类型土壤细菌群落结构和多样性。当土壤微生物有适宜的营养物质、土壤pH和良好的水热条件, 有利于土壤微生物的生长和繁殖。Shi等[47]在北极苔原4种植被类型研究发现土壤细菌群落组成与土壤pH和含水量密切相关, 而当土壤pH和含水量相似时, 土壤氮的组分可能是细菌结构的重要影响因子。
青藏高原是世界上海拔最高、最独特的生态系统, 垫状植被、高寒草甸、沼泽草甸和高寒灌丛为该地区具有区域代表性的植被类型, 研究区土壤具有较高的有机碳含量[48], 土壤微生物是生物地球化学循环的驱动者, 对气候响应与反馈将影响高寒生态系统的稳定[10], 本研究利用Illumina高通量测序技术对祁连山中部4种植被类型土壤微生物群落结构和多样性进行了研究, 得到了一些初步的结论。未来的研究还应围绕不同季节土壤细菌群落组成和功能以及更大取样尺度的研究等方面展开, 以期待更深入地理解高寒生态系统土壤微生物的群落结构组成及其对气候变化的响应。
4 结论综上所述, 高寒祁连山托勒南山阴坡研究区内4种植被类型, 沼泽草甸土壤微生物生物量碳氮最高;土壤细菌最主要的5个优势门类为放线菌门、酸杆菌门、α-变形菌门、厚壁菌门和芽单胞菌门;土壤pH、土壤含水量、土壤有机碳和总氮是影响4种植被类型土壤细菌群落结构和α多样性的主要因素。
| [1] | 曹鹏, 贺纪正. 微生物生态学理论框架. 生态学报, 2015, 35(22): 7263–7273. |
| [2] | 贺纪正, 王军涛. 土壤微生物群落构建理论与时空演变特征. 生态学报, 2015, 35(20): 6575–6583. |
| [3] | Talbot J M, Bruns T D, Taylor J W, Smith D P, Branco S, Glassman S I, Erlandson S, Vilgalys R, Liao H L, Smith M E, Peay K G. Endemism and functional convergence across the North American soil mycobiome. Proceedings of the National Academy of Sciences of the United States of America, 2014, 111(17): 6341–6346. DOI:10.1073/pnas.1402584111 |
| [4] | 李晨华, 张彩霞, 唐立松, 熊正琴, 王保战, 贾仲君, 李彦. 长期施肥土壤微生物群落的剖面变化及其与土壤性质的关系. 微生物学报, 2014, 54(3): 319–329. |
| [5] | 郑燕, 贾仲君. 新一代高通量测序与稳定性同位素示踪DNA/RNA技术研究稻田红壤甲烷氧化的微生物过程. 微生物学报, 2013, 53(2): 173–184. |
| [6] | 陆雅海, 傅声雷, 褚海燕, 杨云锋, 刘占锋. 全球变化背景下的土壤生物学研究进展. 中国科学基金, 2015, 29(1): 19–24. |
| [7] | Zhang W J, Cheng W M, Ren Z P, Gao Y B, Chen J, Li B L, Zhou C H. Simulation of permafrost distributions in the Qilian Mountains using a multi-criteria approach. Cold Regions Science and Technology, 2014, 103: 63–73. DOI:10.1016/j.coldregions.2014.03.010 |
| [8] | 吴玉环, 高谦, 程国栋. 祁连山地区苔类植物的初步研究. 植物研究, 2008, 28(2): 147–150. |
| [9] | 尹宪志, 张强, 徐启运, 薛万孝, 郭慧, 史志娟. 近50年来祁连山区气候变化特征研究. 高原气象, 2009, 28(1): 85–90. |
| [10] | 褚海燕. 高寒生态系统微生物群落研究进展. 微生物学通报, 2013, 40(1): 123–136. |
| [11] | 刘鹄, 赵文智, 何志斌, 张立杰. 祁连山浅山区不同植被类型土壤水分时间异质性. 生态学报, 2008, 28(5): 2389–2394. |
| [12] | 王军德, 李元红, 李赞堂, 高菁, 金彦兆, 胡想全, 黄津辉. 基于SWAT模型的祁连山区最佳水源涵养植被模式研究——以石羊河上游杂木河流域为例. 生态学报, 2010, 30(21): 5875–5885. |
| [13] | 常宗强, 冯起, 司建华, 李建林, 苏永红. 祁连山不同植被类型土壤碳贮量和碳通量. 生态学杂志, 2008, 27(5): 681–688. |
| [14] | 牛赟, 刘贤德, 敬文茂, 雷军, 苗毓新. 祁连山北坡土壤特性与植被垂直分布的关系. 山地学报, 2013, 31(5): 527–533. |
| [15] | 苏永中, 常学向, 何志斌, 王芳. 祁连山典型流域谷地植被斑块演变与土壤性状. 生态学报, 2008, 28(1): 212–219. |
| [16] | 赵成章, 石福习, 董小刚, 任珩, 盛亚萍, 高福元, 杨文斌. 祁连山北坡退化林地植被群落的自然恢复过程及土壤特征变化. 生态学报, 2011, 31(1): 115–122. |
| [17] | 韩春坛, 陈仁升, 刘俊峰, 阳勇, 刘章文. 祁连山葫芦沟流域高山寒漠带非冻结期水文特征. 冰川冻土, 2013, 35(6): 1536–1544. |
| [18] | Chen R S, Song Y X, Kang E S, Han C T, Liu J F, Yang Y, Qing W W, Liu Z W. A cryosphere-hydrology observation system in a small alpine watershed in the Qilian Mountains of China and its meteorological gradient. Arctic, Antarctic, and Alpine Research, 2014, 46(2): 505–523. DOI:10.1657/1938-4246-46.2.505 |
| [19] | 朱平, 陈仁升, 宋耀选, 刘光琇, 陈拓, 张威. 祁连山不同植被类型土壤微生物群落多样性差异. 草业学报, 2015, 24(6): 75–84. DOI:10.11686/cyxb2014272 |
| [20] | 张甘霖, 龚子同. 土壤调查实验室分析方法. 北京:科学出版社, 2012: 23–76. |
| [21] | Brookes P C, Landman A, Pruden G, Jenkinson D S. Chloroform fumigation and the release of soil nitrogen: a rapid direct extraction method to measure microbial biomass nitrogen in soil. Soil Biology and Biochemistry, 1985, 17(6): 837–842. DOI:10.1016/0038-0717(85)90144-0 |
| [22] | Vance E D, Brookes P C, Jenkinson D S. An extraction method for measuring soil microbial biomass C. Soil Biology and Biochemistry, 1987, 19(6): 703–707. DOI:10.1016/0038-0717(87)90052-6 |
| [23] | Mago č T, Salzberg S L. FLASH: fast length adjustment of short reads to improve genome assemblies. Bioinformatics, 2011, 27(21): 2957–2963. DOI:10.1093/bioinformatics/btr507 |
| [24] | Caporaso J G, Kuczynski J, Stombaugh J, Bittinger K, Bushman F D, Costello E K, Fierer N, Peña A G, Goodrich J K, Gordon J I, Huttley G A, Kelley S T, Knights D, Koenig J E, Ley R E, Lozupone C A, McDonald D, Muegge B D, Pirrung M, Reeder J, Sevinsky J R, Turnbaugh P J, Walters W A, Widmann J, Yatsunenko T, Zaneveld J, Knight R. QIIME allows analysis of high-throughput community sequencing data. Nature Methods, 2010, 7(5): 335–336. DOI:10.1038/nmeth.f.303 |
| [25] | Edgar R C. UPARSE: highly accurate OTU sequences from microbial amplicon reads. Nature Methods, 2013, 10(10): 996–998. DOI:10.1038/nmeth.2604 |
| [26] | McDonald D, Price M N, Goodrich J, Nawrocki E P, DeSantis T Z, Probst A, Andersen G L, Knight R, Hugenholtz P. An improved Greengenes taxonomy with explicit ranks for ecological and evolutionary analyses of bacteria and archaea. The ISME Journal, 2012, 6(3): 610–618. DOI:10.1038/ismej.2011.139 |
| [27] | Wang Q, Garrity G M, Tiedje J M, Cole J R. Naïve Bayesian classifier for rapid assignment of rRNA sequences into the new bacterial taxonomy. Applied and Environmental Microbiology, 2007, 73(16): 5261–5267. DOI:10.1128/AEM.00062-07 |
| [28] | Faith D P. Conservation evaluation and phylogenetic diversity. Biological Conservation, 1992, 61(1): 1–10. DOI:10.1016/0006-3207(92)91201-3 |
| [29] | 张金屯. 数量生态学. 北京:科学出版社, 2004: 157–164. |
| [30] | Grandy A S, Strickland M S, Lauber C L, Bradford M A, Fierer N. The influence of microbial communities, management, and soil texture on soil organic matter chemistry. Geoderma, 2009, 150(3/4): 278–286. |
| [31] | Melo V S, Desjardins T, Silva Jr M L, Santos E R, Sarrazin M, Santos M M L S. Consequences of forest conversion to pasture and fallow on soil microbial biomass and activity in the eastern Amazon. Soil Use and Management, 2012, 28(4): 530–535. DOI:10.1111/sum.2012.28.issue-4 |
| [32] | 王启兰, 曹广民, 王长庭. 高寒草甸不同植被土壤微生物数量及微生物生物量的特征. 生态学杂志, 2007, 26(7): 1002–1008. |
| [33] | 孙波, 赵其国, 张桃林, 俞慎. 土壤质量与持续环境——Ⅲ.土壤质量评价的生物学指标. 土壤, 1997, 29(5): 225–234. |
| [34] | Wardle D A. A comparative assessment of factors which influence microbial biomass carbon and nitrogen levels in soil. Biological Reviews, 1992, 67(3): 321–358. DOI:10.1111/brv.1992.67.issue-3 |
| [35] | Janssen P H. Identifying the dominant soil bacterial taxa in libraries of 16S rRNA and 16S rRNA genes. Applied and Environmental Microbiology, 2006, 72(3): 1719–1728. DOI:10.1128/AEM.72.3.1719-1728.2006 |
| [36] | Philippot L, Andersson S G E, Battin T J, Prosser J I, Schimel J P, Whitman W B, Hallin S. The ecological coherence of high bacterial taxonomic ranks. Nature Reviews Microbiology, 2010, 8(7): 523–529. DOI:10.1038/nrmicro2367 |
| [37] | Chu H Y, Sun H B, Tripathi B M, Adams J M, Huang R, Zhang Y J, Shi Y. Bacterial community dissimilarity between the surface and subsurface soils equals horizontal differences over several kilometers in the western Tibetan Plateau. Environmental Microbiology, 2016, 18(5): 1523–1533. DOI:10.1111/1462-2920.13236 |
| [38] | Yuan Y L, Si G C, Wang J, Luo T X, Zhang G X. Bacterial community in alpine grasslands along an altitudinal gradient on the Tibetan Plateau. FEMS Microbiology Ecology, 2014, 87(1): 121–132. DOI:10.1111/1574-6941.12197 |
| [39] | Zhang X F, Zhao L, Xu Jr S J, Liu Y Z, Liu H Y, Cheng G D. Soil moisture effect on bacterial and fungal community in Beilu River (Tibetan Plateau) permafrost soils with different vegetation types. Journal of Applied Microbiology, 2013, 114(4): 1054–1065. DOI:10.1111/jam.2013.114.issue-4 |
| [40] | Yergeau E, Hogues H, Whyte L G, Greer C W. The functional potential of high Arctic permafrost revealed by metagenomic sequencing, qPCR and microarray analyses. The ISME Journal, 2010, 4(9): 1206–1214. DOI:10.1038/ismej.2010.41 |
| [41] | DeBruyn J M, Nixon L T, Fawaz M N, Johnson A M, Radosevich M. Global biogeography and quantitative seasonal dynamics of Gemmatimonadetes in soil. Applied and Environmental Microbiology, 2011, 77(17): 6295–6300. DOI:10.1128/AEM.05005-11 |
| [42] | Rousk J, Bååth E, Brookes P C, Lauber C L, Lozupone C, Caporaso J G, Knight R, Fierer N. Soil bacterial and fungal communities across a pH gradient in an arable soil. The ISME Journal, 2010, 4(10): 1340–1351. DOI:10.1038/ismej.2010.58 |
| [43] | Fierer N, Jackson R B. The diversity and biogeography of soil bacterial communities. Proceedings of the National Academy of Sciences of the United States of America, 2006, 103(3): 626–631. DOI:10.1073/pnas.0507535103 |
| [44] | Lauber C L, Hamady M, Knight R, Fierer N. Pyrosequencing-Based Assessment of Soil pH as a Predictor of Soil Bacterial Community Structure at the Continental Scale. Applied and Environmental Microbiology, 2009, 75(15): 5111–5120. DOI:10.1128/AEM.00335-09 |
| [45] | Shen C C, Xiong J B, Zhang H Y, Feng Y Z, Lin X G, Li X Y, Liang W J, Chu H Y. Soil pH drives the spatial distribution of bacterial communities along elevation on Changbai Mountain. Soil Biology and Biochemistry, 2013, 57: 204–211. DOI:10.1016/j.soilbio.2012.07.013 |
| [46] | Shen C C, Ni Y Y, Liang W J, Wang J J, Chu H Y. Distinct soil bacterial communities along a small-scale elevational gradient in alpine tundra. Frontiers in Microbiology, 2015, 6: 582. |
| [47] | Shi Y, Xiang X J, Shen C C, Chu H Y, Neufeld J D, Walker V K, Grogan P. Vegetation-Associated Impacts on Arctic Tundra Bacterial and Microeukaryotic Communities. Applied and Environmental Microbiology, 2015, 81(2): 492–501. DOI:10.1128/AEM.03229-14 |
| [48] | 杨帆, 黄来明, 李德成, 杨飞, 杨仁敏, 赵玉国, 杨金玲, 刘峰, 张甘霖. 高寒山区地形序列土壤有机碳和无机碳垂直分布特征及其影响因素. 土壤学报, 2015, 52(6): 1226–1236. |
 2017, Vol. 37
2017, Vol. 37