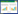文章信息
- 张永敢, 赵娟, 张玉洁, 吴婷, 吴孝兵, 郑艳
- ZHANG Yonggan, ZHAO Juan, ZHANG Yujie, WU Ting, WU Xiaobing, ZHENG Yan.
- 药用植物凤丹(Paeonia suffruticosa)根际土壤细菌群落16S rRNA基因的ARDRA分析
- Bacterial diversity in rhizosphere soil of the medicinal tree peony (Paeonia suffruticosa) revealed by amplified ribosomal DNA restriction analysis
- 生态学报[J]. 2016, 36(17): 5564-5574
- Acta Ecologica Sinica[J]. 2016, 36(17): 5564-5574
- http://dx.doi.org/10.5846/stxb201503030405
-
文章历史
- 收稿日期: 2015-03-03
- 修订日期: 2016-03-21
2. 安徽师范大学生命科学学院, 芜湖 241000
2. School of Life Science, Anhui Normal University, Wuhu 241000, China
凤丹(Paeonia suffruticosa Andr.)又称铜陵牡丹,为芍药科多年生药用植物,是世界上著名的花卉之一,素有“国色天香”之美誉,在中国已有上千年的栽种历史。其根皮可供药用,俗称丹皮,是一种贵重的中药材。我国药用植物凤丹主要分布在河南洛阳,山东菏泽,安徽的亳州、铜陵和南陵,但地道药材凤丹则主产于安徽铜陵和南陵一带。丹皮虽然年产量较高,但是地道药材丹皮所占的比重却较少,近年来市场上对高质量丹皮的需求不断增加[1],而影响丹皮质量的因素却非常之多。目前,对凤丹的研究主要集中在品种[2]、化学成分与药理药效[3-4]、生理生化[5-6]、病虫害防治[7]及丹皮的储存加工[8]等方面,而对凤丹根际土壤微生物的群落结构和丰富度的研究相对缺乏,如康业斌等[9]利用HPLC法和涂布平板法研究了凤丹和洛阳红根际微生物及其与根皮中丹皮酚含量的关系,结果发现,洛阳红根际土壤中微生物数量明显高于凤丹,但其根皮中丹皮酚含量却低于凤丹;Han等[10]利用传统纯培养的方法研究了牡丹(Paeonia ostii)根部土壤微生物的多样性,结果发现,不同牡丹品系(蓝芙蓉、凤丹)的根部细菌群落结构有明显的差异性;Xue和Huang[11]利用了聚合酶链式反应-变性梯度凝胶电泳法(polymerase chain reaction-denaturing gradient gel electrophoresis,PCR-DGGE)研究了牡丹根部土壤微生物群落结构及其与牡丹品系和种植年限的变化关系,结果发现,牡丹品系和种植年限均会影响土壤微生物群落结构并且后者高于前者。
土壤微生物是土壤生态系统的重要组成部分,其在物质循环、能量流动及有机质分解等方面发挥着至关重要的作用[12]。土壤中存在大量的根际促生菌(PGPR)和部分有害细菌(DRB)及植物病原菌。 PGPR定殖于植物根际土壤中,通过产生植物激素[13] 、提高营养成分[14]、抑制DRB和植物病原菌[15-16]等来促进植物的生长发育;与之相反,土壤中的DRB和植物病原菌通过侵染植物维管组织、产生微生物毒素及与其他微生物间相互作用[17],影响植物的健康生长。所以,研究根际土壤微生物的群落多样性及其群落结构在植物的生长和健康等方面是至关重要的[18]。
扩增核糖体DNA限制性内切酶分析法(amplified ribosomal DNA restriction analysis,ARDRA)是基于特异限制性内切酶对一定长度的DNA片段进行酶切,酶切产物通过琼脂糖凝胶电泳进行分离和检测,从而分析环境微生物的多样性。由于该技术不受菌株能否纯培养的限制,不受宿主的干扰,具有特异性强、效率高、试验结果稳定、可重复性好等优点[19],已被广泛地用于环境微生物多样性和系统发育关系的研究。本研究采用PCR技术,从凤丹(P. suffruticosa)根际土壤微生物的总DNA中选择性地扩增细菌群落的16S rRNA基因片断,在此基础上构建细菌的16S rRNA基因克隆文库,然后利用ARDRA法对其进行分析,从而建立凤丹栽培土壤微生物种群遗传多样性ARDRA研究体系,揭示其根际细菌群落结构及多样性特征,为研究药材的地道性与土壤微生物之间的关系奠定基础。
1 材料与方法 1.1 土壤样品的采集和理化分析于2012年4月在安徽铜陵(FH)、芜湖(YS)、亳州(BZ)、山东菏泽(HZ)和河南洛阳(LY)采集3年生凤丹的根际土壤样品(图 1和表 1)。在株龄为3a的凤丹栽植区内随机选取3株凤丹,除去表层土壤,挖掘出带根整体植株,把附着在根系上的土壤抖落下来,作为根际土,每株凤丹根际土壤取样量大体一致,将采集的土壤装入灭菌的封口聚乙烯袋中,带回实验室于-20℃保存备用。使用全球定位系统(GPS)测定了采样点的经纬度;利用pH计测量土壤样品的pH值(土壤∶水=1∶2.5);土壤总磷(TP)和总钾(TK)经过酸消解[HNO3 (65%)∶ HF (40%) =9∶4,体积分数]后,使用ICP-OES (optic emission spectroscopy with inductively coupled plasma)进行测定[20];土壤总铜(TCu)和总锌(TZn)经过酸消解(HNO3∶HClO4 = 4∶1,体积分数)后,使用原子吸收分光光度法测定[21];其他参数为土壤总有机碳(TOC)(重铬酸钾氧化法)[22]和土壤总氮(TN)(凯氏定氮法)[23]。
|
| 图 1 药用植物凤丹(Paeonia suffruticosa)根际土壤样品采集点地图 Fig. 1 The map of sampling sites of rhizosphere soil from medicinal tree peony (Paeonia suffruticosa) of variety (Fengdan) |
将每个采样点的3份平行土壤样品均匀混合后,采用试剂盒FastDNASPIN Kit for Soil(MP Biomedicals,CA,USA),根据生产商提供的方法提取土壤微生物基因组DNA,提取的结果用经EB(ethidium bromide)染色的1%(w/v)的琼脂糖凝胶电泳进行检测。
使用基因扩增仪PTC-200(MJ Research Inc,Watertown,MA,USA),以细菌引物F27 [5′-AGAGTTTGATCMTGGCTCAG-3′ E. coli bases 8-27]和R1487 [5′-ACGGTTACCTTGTTACGACTT-3′ E. coli bases 1487—1507][24]扩增土壤细菌16S rRNA 基因。PCR的反应体系为30μL,包括10mmol/L的Tris-HCl (pH 8.3),50mmol/L KCl,1.5mmol/L MgCl2,0.25mmol/L dNTP,1U Taq酶(TaKaRa Biotechnology),1μg BSA(bovine serum albumin),50ng DNA 模版和引物各10μmol/L。PCR的反应条件为:94℃预变性10min,94℃变性45s,50℃退火1s,72℃延伸1min,30个循环,最后72℃延伸10min。PCR产物用含有EB的1% 的琼脂糖凝胶电泳检测。
1.3 16S rRNA基因文库构建采用DNA凝胶纯化试剂盒[AxyPrepTM PCR Cleanup Kit (AXYGEN Biotechnology (Hangzhou) Limited,Hangzhou,China)]纯化扩增后的产物,之后将纯化产物通过连接试剂盒(TaKaRa,Dalian,China)连接到载体上,再将连接产物转化到大肠杆菌(DH5α)的感受态细胞中,均匀涂布到含有氨苄青霉素(100μg/mL)、X-gal(5-bromo-4-chloro-3-indolyl β-D-galactopyranoside)(40μg/mL)和IPTG(isopropyl β-D-thiogalactopyranoside)(24μg/mL)的LB(Luria-Bertani)培养基上。每个土壤样品随机挑选了200个白色克隆子,并使用pMD18-T easy vector通用引物M13(-47)[5′-AGGGTTTTCCCAGTCACG-3′] 和M13(-48)[5′-GAGCGGATAACAATTTCA CAC-3′] 扩增外源插入片断,将插入片断的克隆子进行ARDRA分析。
1.4 ARDRA分析以限制性内切酶HinfI 和 Csp6I(Fermentas,AM)酶切上述从各个克隆子扩增出来的16S rRNA基因片断。双酶切的反应体系为:2μL 1×TangoTM酶切反应缓冲液,限制性内切酶HinfI 和 Csp6I各1μL(10U),10μL(约 0.5μg DNA)PCR产物,最后加灭菌水至30μL,37℃过夜消化,最后经 65℃ 水浴20min,终止酶切反应。酶切产物用经EB染色的2%(w/v)琼脂糖凝胶电泳检测,得到的酶切谱型图,利用软件GelComparv. 3.0 (Applied Math,Kortrijk,Belgium)进行分析,小于100bp的片段比较模糊,在本研究中不计数。
1.5 部分克隆子的16S rRNA基因测序根据ARDRA谱型分析,将克隆文库中的优势酶切谱型(>3个克隆子)挑选一个克隆子送交上海生工生物技术有限公司进行测序。
1.6 数据分析以稀疏曲线(http://www.uga.edu/strata/software/anRareReadme.html)和Coverage C[25]评价所构建的克隆文库的库容;采用Shannon-Wiener多样性指数(H′)和均匀度指数(EH)[11]及Chao1指数[26]进行多样性分析;16S rRNA基因序列经软件ContigExpress (version,June 20,2000) 拼接,用Mallard[27]进行嵌合体检查,剩下的序列利用RDP II(http://rdp.cme.msu.edu/classifier/classifie)和NCBI BLASTN(http://blast.ncbi.nlm.nih.gov/)分析后,用软件Clustal X (1.81) 和MEGA 5.0 (Molecular Evolutionary Genetics Analysis,MEGA) 构建系统发育树(Neighbor-joining tree)。
2 结果与分析 2.1 土壤理化性质5个采样点凤丹根际土壤的理化性质见表 1。所测的土壤pH值范围为6.04—6.62,趋于中性。TOC和TN在YS最高,其次是HZ、LY、BZ,FH最低,TP在BZ最高(0.978g/kg),FH最低(0.536g/kg),TK、TZn和TCu的浓度范围分别为:17.499—19.669g/kg、0.077—0.139g/kg和0.015—0.029g/kg。
| 样品编号Sample No. | 采样地点Sampling location | 经纬度Latitude & attitude | pH | 有机质Organic C/(g/kg) | 总氮Total N/(g/kg) | 总磷Total P/(g/kg) | 总钾Total K/(g/kg) | 总锌Total Zn/(g/kg) | 总铜Total Cu/(g/kg) |
| FH | 安徽省铜陵市铜陵县钟鸣镇 | 118°03′28″E30°58′47″N | 6.04d | 19.107c | 0.777c | 0.536e | 18.731c | 0.139a | 0.022b |
| YS | 安徽省芜湖市南陵县河湾镇 | 118°05′04″E30°48′53″N | 6.62a | 29.861a | 1.221a | 0.778c | 19.041b | 0.107b | 0.029a |
| BZ | 安徽省亳州市谯城区十八里镇 | 115°39′58″E33°52′11″″N | 6.09cd | 17.051d | 0.693d | 0.978a | 19.669a | 0.085d | 0.018c |
| HZ | 山东省菏泽市牡丹区小留镇 | 115°26′04″E35°21′15″N | 6.43b | 10.125e | 0.408e | 0.794b | 19.661a | 0.077e | 0.015d |
| LY | 河南省洛阳市老城区邙山镇 | 112°23′30″E34°42′30″N | 6.20c | 19.562b | 0.798b | 0.633d | 17.499d | 0.100c | 0.029a |
| P<0.05水平下 LSD检验,相同的字母代表差异不显著的同一组 | |||||||||
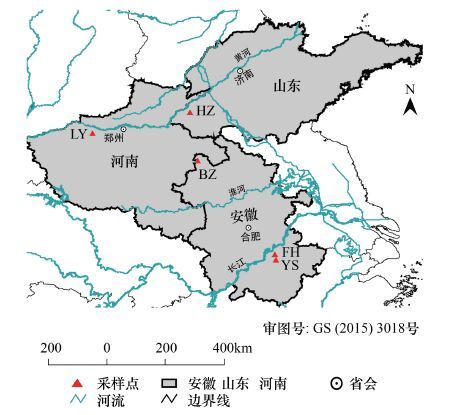
对从5个样品中随机挑选的1000个白色克隆子进行PCR扩增获得其外源插入片断,然后进行双酶切。酶切结果显示,库中的ARDRA谱型包含2—6个条带,条带大小范围在100—1302bp(图 2)。用NTSYSpc 2.10e进行聚类分析,将具有相同ARDRA谱型的克隆子归为同一种可操作分类单元(OTU)[28]。聚类分析结果显示702个含有外源插入片段的克隆子被聚为324个OTUs,FH、YS、BZ、HZ、LY分别包含74、69、76、73、72个OTUs,其中含有1、2、3个克隆子的OTU分别占所有被分析16S rRNA基因克隆子的26%、23% 和18%,优势ARDRA谱型(>3个克隆子)有38个,占所有被分析16S rRNA基因克隆子的33%(图 3)。
|
| 图 2 凤丹根际土壤16S rRNA基因文库中部分克隆的酶切图谱(a.从克隆子中扩增出的16S rRNA基因插入片断,b.经HinfI和Csp6I消化产生的片断多态性) Fig. 2 16S rRNA gene enzyme digestion process (a. Inserted 16S rRNA gene from clones,b. RFLP profiles of some clones digested by HinfI and Csp6I) |
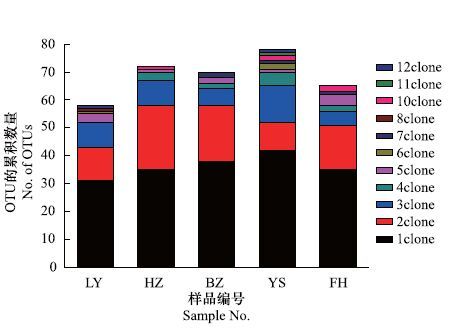
|
| 图 3 五个克隆文库中细菌群落16S rRNA基因克隆的ARDRA型分布 Fig. 3 ARDRA distribution in five 16S rRNA gene clone libraries from bacteria community |
所构建的5个凤丹根际土壤细菌群落的16S rRNA基因文库的Coverage C为71.32— 81.40,均大于70% 且YS(81.40%)明显高于其他4个(表 2)。稀疏曲线分析结果见图 4。克隆文库的多样性指数分析显示,FH、YS、BZ、HZ、LY克隆文库的Shannon-Wiener多样性指数(H′)依次分别为4.141、3.949、4.173、4.184和4.120。均匀度指数(EH)范围为0.933—0.975且YS(0.933)明显小于其他4个。Chao1指数YS最高(107.25),HZ最低(89.52)。
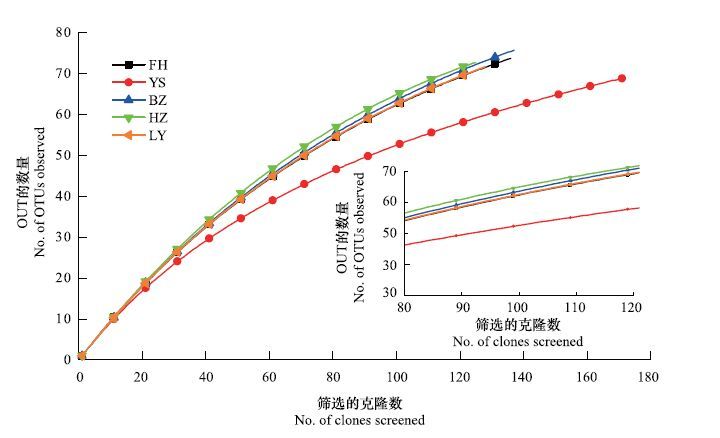
|
| 图 4 凤丹根际土壤细菌群落16S rRNA 基因克隆文库的稀疏曲线分析 Fig. 4 Rarefaction curves generated for 16S rRNA genes in clones libraries from soil samples collected in YS,FH,BZ,HZ and LY,indicating the observed number of operational taxonomic units (OTUs) at a genetic distance of 3% |
| 样品名称Soil sample | 克隆数No. of clones | 覆盖度Coverage/% | Shannon指数Shannon diversity index (H′) | 丰度Richness(NO. of OTUs) | 均匀度Evenness (EH) | Chao1指数Chao1 index (SChao1) |
| FH | 132 | 73.72 | 4.141 | 74 | 0.962 | 95.75 |
| YS | 172 | 81.40 | 3.949 | 69 | 0.933 | 107.25 |
| BZ | 138 | 72.46 | 4.173 | 76 | 0.964 | 103.07 |
| HZ | 126 | 73.81 | 4.184 | 73 | 0.975 | 89.52 |
| LY | 129 | 71.32 | 4.120 | 72 | 0.963 | 99.78 |
| 样品FH、YS、BZ、HZ、LY,分别表示采自于铜陵、芜湖、亳州、菏泽、洛阳牡丹园内3年生4月份凤丹根际土壤 | ||||||
为了更详细了解凤丹根际土壤的优势细菌种类组成,从库中占优势的ARDRA谱型中挑选了38个代表克隆子,对其插入的16S rRNA基因片段进行测序,并建立系统发育树(图 5)。优势OTU所代表的细菌类群详细描述见表 3,主要包括变形菌门(Proteobacteria)的alpha、beta、gamma、delta 亚门,酸杆菌门(Acidobacteria),放线菌门(Actinobacteria),拟杆菌门(Bacteroidetes)及厚壁菌门(Firmicutes)等11类细菌,此外,还包含了3个未归类的细菌。克隆文库中16S rRNA基因序列相似性为95%—99%,其最相似细菌主要来自花生、向日葵、草原、森林等不同类型的土壤。
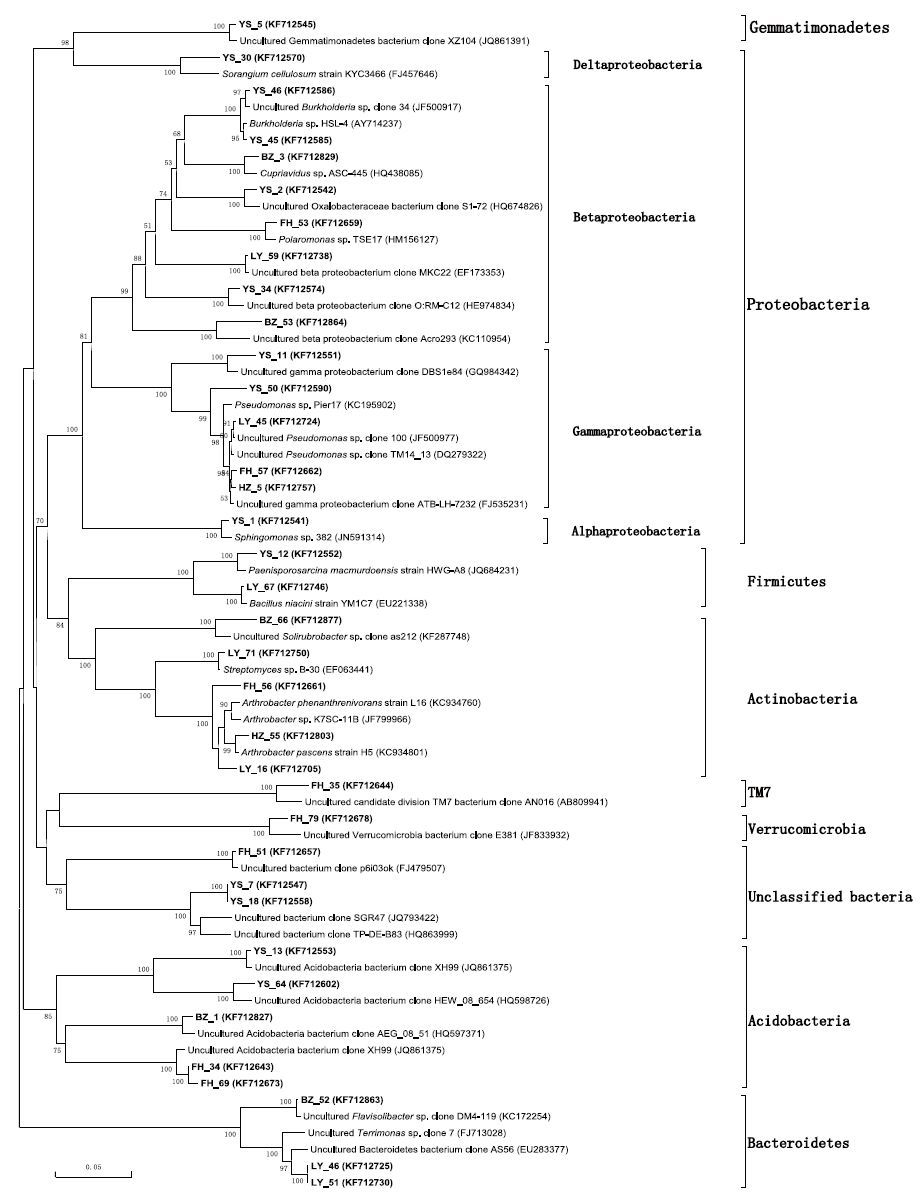
|
| 图 5 基于16S rRNA基因序列同源性的38个优势OTUs系统发育树 Fig. 5 Phylogenetic tree showing the relationship of 16S rRNA gene sequences of 38 dominant OTUs compared with the most similar GenBank sequences. The tree was constructed by the use of neighbor-joining analysis based on rRNA gene sequences. Only bootstrap values (n=1000 replicates) above 50% were displayed and the par represents a 0.05 of nucleotide divergence. All the sequences highlighted in bold were retrieved from this study |
| 克隆编号Clone no. | 代表克隆数Clones represented | 与NCBI中最相似序列(登录号)Closest NCBI match(Accession no.) | 生境Habitat-Ecological niche | 相似性%Identity | 分类Taxon |
| FH_34 | 5 | Uncultured Acidobacteria bacterium clone XH99(JQ861375) | peanut rhizosphere soil | 98 | Acidobacteria |
| FH_69 | 5 | Uncultured Acidobacteria bacterium clone XH99(JQ861375) | peanut rhizosphere soil | 97 | Acidobacteria |
| YS_13 | 7 | Uncultured Acidobacteriaceae bacterium clone CS6(JQ771962) | sunflower rhizosphere; creosote polluted soil | 98 | Acidobacteria |
| YS_64 | 4 | Uncultured Acidobacteria bacterium clone HEW_08_654(HQ598726) | woodland soil | 97 | Acidobacteria |
| BZ_1 | 7 | Uncultured Acidobacteria bacterium clone AEG_08_51(HQ597371) | grassland soil | 99 | Acidobacteria |
| FH_56 | 4 | Arthrobacter phenanthrenivorans strain L16(KC934760) | purple siltstone | 98 | Actinobacteria |
| BZ_66 | 4 | Uncultured Solirubrobacter sp. clone as212(KF287748) | water from a copper mine | 96 | Actinobacteria |
| HZ_55 | 5 | Arthrobacter pascens strain H5(KC934801) | purple siltstone | 99 | Actinobacteria |
| LY_16 | 5 | Arthrobacter sp. K7SC-11B(JF799966) | soil | 98 | Actinobacteria |
| LY_71 | 5 | Streptomyces sp. B-30(EF063441) | unreported | 99 | Actinobacteria |
| YS_1 | 6 | Sphingomonas sp. 382(JN591314) | prealpine freshwater lake | 98 | Alphaproteobacteria |
| BZ_52 | 5 | Uncultured Flavisolibacter sp. clone DM4-119(KC172254) | ginger continuous cropping soil | 99 | Bacteroidetes |
| LY_46 | 5 | Uncultured Bacteroidetes bacterium clone AS56(EU283377) | activated sludge from membrane bioreactor | 98 | Bacteroidetes |
| LY_51 | 4 | Uncultured Terrimonas sp. clone 7(FJ713028) | groundwater contaminated with MTBE | 97 | Bacteroidetes |
| FH_53 | 4 | Polaromonas sp. TSE17(HM156127) | soil from glacier forefield | 98 | Betaproteobacteria |
| YS_2 | 11 | Uncultured Oxalobacteraceae bacterium clone S1-72(HQ674826) | variably weathered outcrop | 98 | Betaproteobacteria |
| YS_34 | 5 | Uncultured beta proteobacterium clone O:RM-C12(HE974834) | Ajka red mud contaminated soils | 98 | Betaproteobacteria |
| YS_45 | 4 | Burkholderia sp. HSL-4(AY714237) | soil | 99 | Betaproteobacteria |
| YS_46 | 6 | Uncultured Burkholderia sp. clone 34(JF500917) | rye-grass rhizosphere | 99 | Betaproteobacteria |
| BZ_3 | 4 | Cupriavidus sp. ASC-445(HQ438085) | agricultural rhizosphere soil | 98 | Betaproteobacteria |
| BZ_53 | 5 | Uncultured beta proteobacterium clone Acro293(KC110954) | Acrobeloides maximus in soil microcosm | 95 | Betaproteobacteria |
| LY_59 | 4 | Uncultured beta proteobacterium clone MKC22(EF173353) | hydrocarbon-contaminated soil | 99 | Betaproteobacteria |
| YS_30 | 4 | Sorangium cellulosum strain KYC3466(FJ457646) | unreported | 95 | Deltaproteobacteria |
| YS_12 | 4 | Paenisporosarcina macmurdoensis strain HWG-A8(JQ684231) | permafrost soil samples | 98 | Firmicutes |
| LY_67 | 5 | Bacillus niacini strain YM1C7(EU221338) | wheat rhizosphere | 99 | Firmicutes |
| FH_57 | 4 | Uncultured Pseudomonas sp. clone TM14_13(DQ279322) | Tuber magnatum | 99 | Gammaproteobacteria |
| YS_11 | 6 | Uncultured gamma proteobacterium clone DBS1e84(GQ984342) | surface water in the Northern Bering Sea | 98 | Gammaproteobacteria |
| YS_50 | 4 | Pseudomonas sp. Pier17(KC195902) | heavy metal contaminated soil | 96 | Gammaproteobacteria |
| HZ_5 | 4 | Uncultured gamma proteobacterium clone ATB-LH-7232(FJ535231) | washing water of carrot washing plant | 99 | Gammaproteobacteria |
| LY_45 | 5 | Uncultured Pseudomonas sp. clone 100(JF500977) | rye-grass rhizosphere | 99 | Gammaproteobacteria |
| YS_5 | 10 | Uncultured Gemmatimonadetes bacterium clone XZ104(JQ861391) | peanut rhizosphere soil | 99 | Gemmatimonadetes |
| FH_35 | 6 | Uncultured candidate division TM7 bacterium clone AN016(AB809941) | acidophilic nitrifying activated sludge | 97 | TM7 |
| FH_51 | 4 | Uncultured bacterium clone p6i03ok(FJ479507) | undisturbed tall grass prairie,top 5 cm | 99 | Unclassified bacteria |
| YS_7 | 8 | Uncultured bacterium clone SGR47(JQ793422) | rhizosphere of Arachis hypogaea | 95 | Unclassified bacteria |
| YS_18 | 4 | Uncultured bacterium clone TP-DE-B83(HQ863999) | alpine meadow in the upper area of Shule River | 95 | Unclassified bacteria |
| FH_79 | 5 | Uncultured Verrucomicrobia bacterium clone E381(JF833932) | potassium mine soil | 97 | Verrucomicrobia |
在测序的优势代表克隆子中,有15个属于变形细菌,代表了15个OTUs,其中α-、β-、γ-、δ-Proteobacteria分别为1、8、5、1个。在γ-Proteobacteria的5个OTUs中,丰度最高的克隆子(13个)代表了与Pseudomonas sp. 相近的3个OTUs,序列相似性为96%—99%,为文库优势菌属。在β-Proteobacteria的8个OTUs中,有2个OTUs(含有10个克隆子)与Burkholderia sp. 相近,16S rRNA基因序列相似性为99%,为文库优势菌属。此外,有2个OTUs分别与Polaromonas sp. 和Cupriavidus sp. 相近,序列相似性为98%。在与变形细菌相似的OTU中,仅有1个OTU与α-Proteobacteria的Sphingomonas sp. 聚为一群,序列相似性为98%。而与δ-Proteobacteria相近的1个OTU与已知的Sorangium cellulosum strain KYC3466的序列相似性为95%。
2.4.2 酸杆菌门(Acidobacteria)有5个OTUs与酸杆菌门的细菌聚为一群(图 5),共包含了28个克隆子,均为不可培养的细菌,16S rRNA基因序列相似性为97%—99%。
2.4.3 放线菌(Actinobacteria)在放线菌的5个OTUs中,丰度最高的克隆子(14个)代表了与Arthrobacter sp. 相近的3个OTUs,序列相似性为98%—99%,为文库优势菌属。其余2个OTUs分别于Solirubrobacter sp. 和Streptomyces sp. 相近,16S rRNA基因序列相似性为96%—99%。
2.4.4 其他细菌有3个OTUs与拟杆菌门的细菌聚在一起(图 5),序列相似性为97%—99%。2个 OTUs分别以98%和99%的相似水平与从土壤中分离到的厚壁菌门菌株Paenisporosarcina macmurdoensis和Bacillus niacini聚在一起。分别有1个OUT与芽单胞菌门(Gemmatimonadetes)、TM7菌和疣微菌门(Verrucomicrobia)聚在一起。
3 讨论16S rRNA基因克隆文库的构建是微生物分子生态学中用来研究环境中微生物多样性的主要方法之一[29]。通过对文库中的克隆进行测序,了解环境样品中的微生物组成。但是要获得一个较全面、详细的微生物群落组成分析结果,就需要建一个足够大的文库,而对文库中每个克隆进行测序,就需要高昂的费用[30]。ARDRA不但可以快速、稳定地分析微生物群落组成,而且可以减少测序费用[31]。为了验证ARDRA的分析结果,随机挑选了5种谱型,每种谱型送2—3个克隆子进行序列测定,结果表明来自同一种谱型不同克隆子的序列是一样的。通过ARDRA分析,702个阳性克隆子被聚为324个OTUs,这样测序量就大大降低。通过对谱型图的观察分析发现,不同类型的细菌具有不同的谱型,这表明所使用的限制性内切酶HinfI和Csp6I可以很好地区分所研究的细菌种群。此外,大部分的谱型只包含了1—3个克隆,说明凤丹根际土壤具有丰富的细菌多样性。
为了对凤丹根际土壤细菌群落做一个较全面的分析,本研究中使用了稀疏曲线和Coverage C[25]来评价所构建的克隆文库大小。Coverage C越高,表明所构建的文库越能代表环境中的细菌群落多样性。结果显示,所构建的5个凤丹根际土壤细菌群落的16S rRNA基因文库的Coverage C均大于70%(表 2),说明所构建的克隆文库基本可以反映所采集土壤细菌群落的多样性,这一结果与稀疏曲线分析一致(图 4)。此外,YS的Coverage C明显高于其他4个,表明YS未被检测到的微生物最少,最能反应其土壤细菌群落的多样性。
细菌多样性分析结果显示,虽然YS的Chao1指数最高(107.25),但是其均匀度(EH)和Shannon-Wiener多样性指数(H′)却最低(0.933和3.949)(表 2)。这可能因为Chao1指数用于反映物种丰富度的非参数估计[26],而Shannon-Wiener多样性指数不仅反映了物种的丰富度,而且反映了其均匀度[32]。与前人相似的研究比较发现,使用分子方法研究微生物多样性[11]比使用传统纯培养方法[10]获得的细菌多样性指数要高。凤丹地道产区(FH和YS)与非地道产区(BZ、HZ和LY)的细菌群落都具有较高的多样性(表 2),这可能与药用植物凤丹在生长发育的周期中形成的特殊根际土壤微环境有关[11] 。
由于优势细菌种类可能对碳、氮循环和其他地球生物化学循环产生较大的影响,因此,了解所研究环境的优势细菌种群是至关重要的。此外,对于特定的细菌主导着微生物群落一直是生态学研究的根本问题[33]。本研究中挑选了优势细菌种群进行测序,并对其进行系统发育分析,结果表明,凤丹根际土壤的优势细菌种群主要包括变形菌门的alpha、beta、gamma、delta亚门,酸杆菌门,放线菌门,拟杆菌门及厚壁菌门等11类细菌,此外,还包含了3个未归类的细菌。其中Pseudomonas sp.、Burkholderia sp. 和Arthrobacter sp.为优势菌属。Pseudomonas是土壤中最常见的细菌,也是根际土壤细菌群落的主要成员之一,具有抑制植物病原菌、促进植物生长的作用[34]。可能因为研究方法不同,Han等[10]利用传统纯培养的方法研究了牡丹(P. ostii)根部土壤微生物的多样性,却没有发现Pseudomonas。Burkholderia是β-Proteobacteria中最丰富的一个属,在矿石风化和氮固定方面具有重要作用[35]。Arthrobacter是放线菌中最主要的一个属,广泛的存在于土壤中。该属的许多种类在不同植物的土壤微生物区系中占优势地位[36],并参与有毒金属(包括铜、锰、镍和铅)的生物吸附[37]。值得注意的是:(1)克隆文库中存在大量未归类的细菌种类,这可能与凤丹根际土壤形成的特殊微环境有关[11];(2)仅在TCu含量最高YS和LY发现了厚壁菌门的细菌优势菌属,这一结果与前人研究结论相一致[38];(3)凤丹地道产区(FH和YS)与非地道产区(BZ、HZ和LY)根际土壤细菌优势菌群均为变形菌门(包括alpha、beta、gamma、detla 亚门)、酸杆菌门、放线菌门,这可能是因为这些优势菌群普遍存在于种植凤丹的根际土壤中。为了更深入地研究凤丹地道产区与非地道产区根际细菌群落间的差异,后续将所有剩下的OTUs进行测序和系统发育分析。
4 结论目前,16S rRNA基因克隆文库和ARDRA方法已广泛应用于生物群落结构和多样性研究中。该方法体系可以反映群落基因组的遗传信息和单个菌株的系统发育信息,但是,要获得较全面的群落结构信息,就需要进行大量样品分析,以确保所构建的克隆文库库容达到要求。
我国药用植物凤丹(P. suffruticosa)主要分布区域的根际土壤细菌种群有11类和3个未归类细菌,其中变形菌门和酸杆菌门为文库中的主要菌群,Pseudomonas sp.、Burkholderia sp. 和Arthrobacter sp. 为优势菌属。表明我国药用植物凤丹(P. suffruticosa)主要分布区域的根际土壤细菌种群不仅具有丰富的多样性,还存在丰富的潜在新种类。
| [1] | He L X, Suo Z L, Zhang C H, Jin X B, Zhao D X, Zhao X Q, Hou B X, Deng C F. Classification of Chinese medicinal tree peony cultivars based on chloroplast DNA sequences. AASRI Procedia , 2012, 1 : 344–352. DOI:10.1016/j.aasri.2012.06.053 |
| [2] | Guo D L, Hou X G, Zhang J. Sequence-related amplified polymorphism analysis of tree peony (Paeonia suffruticosa Andrews) cultivars with different flower colours. Journal of Horticultural Science & Biotechnology , 2009, 84 : 131–136. |
| [3] | Han X Y, Wang L S, Shu Q Y, Liu Z A, Xu S X, Tetsumura T. Molecular characterization of tree peony germplasm using sequence-related amplified polymorphism markers. Biochemical Genetics , 2008, 46 (3/4) : 162–179. |
| [4] | Wu M J, Gu Z Y. Screening of bioactive compounds from Moutan Cortex and their anti-inflammatory activities in Rat Synoviocytes. Evidence-Based Complementary and Alternative Medicine , 2009, 6 (1) : 57–63. DOI:10.1093/ecam/nem066 |
| [5] | 覃逸明, 聂刘旺, 黄雨清, 王千, 刘欣, 周科. 凤丹(Paeonia ostii T.)自毒物质的检测及其作用机制. 生态学报 , 2009, 29 (3) : 1153–1160. |
| [6] | Liu Y L, Xia Y, Guo P, Wang G P, Shen Z G, Xu Y C, Chen Y H. Copper and bacterial diversity in soil enhance paeonol accumulation in Cortex Moutan of Paeonia suffruticosa ‘Fengdan’. Horticulture, Environment, and Biotechnology , 2013, 54 (4) : 331–337. DOI:10.1007/s13580-013-0049-3 |
| [7] | 康业斌, 商鸿生, 成玉梅. 牡丹病害及其固有的化学抗病物质研究进展. 西北农林科技大学学报:自然科学版 , 2005, 33 (8) : 247–249. |
| [8] | 易建利. 储存时间对牡丹皮药材和饮片中丹皮酚含量的影响. 湖南中医药大学学报 , 2008, 28 (3) : 42–43. |
| [9] | 康业斌, 商鸿生, 董苗菊. 凤丹与洛阳红根际微生物及其与根皮中丹皮酚含量的关系. 西北农林科技大学学报:自然科学版 , 2006, 34 (12) : 159–162. |
| [10] | Han J G, Song Y, Liu Z G, Hu Y H. Culturable bacterial community analysis in the root domains of two varieties of tree peony (Paeonia ostii). Fems Microbiology Letters , 2011, 322 (1) : 15–24. DOI:10.1111/fml.2011.322.issue-1 |
| [11] | Xue D, Huang X D. Changes in soil microbial community structure with planting years and cultivars of tree peony (Paeonia suffruticosa). World Journal of Microbiology and Biotechnology , 2014, 30 (2) : 389–397. DOI:10.1007/s11274-013-1457-3 |
| [12] | Bastida F, Kandeler E, Moreno J L, Ros M, García C, Hernández T. Application of fresh and composted organic wastes modifies structure, size and activity of soil microbial community under semiarid climate. Applied Soil Ecology , 2008, 40 (2) : 318–329. DOI:10.1016/j.apsoil.2008.05.007 |
| [13] | Davies P J. The plant hormones:Their nature, occurrence, and functions//Plant Hormones-Biosynthesis, Signal Transduction, Action, 3rd ed. The Netherlands:Springer, 2010:1-15. |
| [14] | Berg G. Plant-microbe interactions promoting plant growth and health:Perspectives for controlled use of microorganisms in agriculture. Applied Microbiology and Biotechnology , 2009, 84 (1) : 11–18. DOI:10.1007/s00253-009-2092-7 |
| [15] | Zhou H Y, Wei H L, Liu X L, Wang Y, Zhang L Q, Tang W H. Improving biocontrol activity of Pseudomonas fluorescens through chromosomal integration of 2,4-diacetylphloroglucinol biosynthesis genes. Chinese Science Bulletin , 2005, 50 (8) : 775–781. |
| [16] | Franke-Whittle I H, Knapp B A, Fuchs J, Kaufmann R, Insam H. Application of COMPOCHIP microarray to investigate the bacterial communities of different composts. Microbial Ecology , 2009, 57 (3) : 510–521. DOI:10.1007/s00248-008-9435-2 |
| [17] | Benizri E, Piutti S, Verger S, Pagès L, Vercambre G, Poessel J L, Michelot P. Replant diseases:Bacterial community structure and diversity in peach rhizosphere as determined by metabolic and genetic fingerprinting. Soil Biology & Biochemistry , 2005, 37 (9) : 1738–1746. |
| [18] | Milling A, Smalla K, Maidl F X, Schloter M, Munch J C. Effects of transgenic potatoes with an altered starch composition on the diversity of soil and rhizosphere bacteria and fungi. Plant and Soil , 2005, 266 (1/2) : 23–39. |
| [19] | Kirk J L, Beaudette L A, Hart M, Moutoglis P, Klironomos J N, Lee H, Trevors J T. Methods of studying soil microbial diversity. Journal of Microbiological Methods , 2004, 58 (2) : 169–188. DOI:10.1016/j.mimet.2004.04.006 |
| [20] | Sardans J, Peñuelas J, Prieto P, Estiarte M. Drought and warming induced changes in P and K concentration and accumulation in plant biomass and soil in a Mediterranean shrubland. Plant and Soil , 2008, 306 (1/2) : 261–271. |
| [21] | Lee C S, Li X D, Shi W Z, Cheung S C, Thornton I. Metal contamination in urban, suburban, and country park soils of Hong Kong:A study based on GIS and multivariate statistics. Science of the Total Environment , 2006, 356 (1/3) : 45–61. |
| [22] | Nelson D W, Sommers L E. Total carbon, organic carbon, and organic matter//Sparks D L, Page A L, Helmke P A, Loeppert R H, Soltanpour P N, Tabatabai M A, Johnson C T, Sumner M E, eds. Methods of Soil Analysis. Part 3-Chemical Methods. Madison:Soil Science Society of America Inc., 1996:961-1010. |
| [23] | Keeney D, Nelson D. Nitrogen-inorganic forms//Page A L, Miller R H, Keeney D R, eds. Methods of Soil Analysis. Part 2. Chemical and Microbiological Properties. American Society of Agronomy, 1982:643-698. http://www.sciepub.com/reference/100744 |
| [24] | Zhao J, Wu X B, Nie C P, Wu T, Dai W H, Liu H, Yang R Y. Analysis of unculturable bacterial communities in tea orchard soils based on nested PCR-DGGE. World Journal of Microbiology and Biotechnology , 2012, 28 (5) : 1967–1979. DOI:10.1007/s11274-011-0999-5 |
| [25] | Good I J. The population frequencies of species and the estimation of population parameters. Biometrika , 1953, 40 (3/4) : 237–264. DOI:10.2307/2333344 |
| [26] | Chao A. Estimating the population size for capture-recapture data with unequal catchability. Biometrics , 1987, 43 (4) : 783–791. DOI:10.2307/2531532 |
| [27] | Ashelford K E, Chuzhanova N A, Fry J C, Jones A J, Weightman A J. New screening software shows that most recent large 16S rRNA gene clone libraries contain chimeras. Applied and Environmental Microbiology , 2006, 72 (9) : 5734–5741. DOI:10.1128/AEM.00556-06 |
| [28] | Moyer C L, Dobbs F C, Karl D M. Estimation of diversity and community structure through restriction fragment length polymorphism distribution analysis of bacterial 16S rRNA genes from a microbial mat at an active, hydrothermal vent system, Loihi Seamount, Hawaii. Applied and Environmental Microbiology , 1994, 60 (3) : 871–879. |
| [29] | Amann R I, Ludwig W, Schleifer K H. Phylogenetic identification and in situ detection of individual microbial cells without cultivation. Microbiology and Molecular Biology Reviews , 1995, 59 (1) : 143–169. |
| [30] | Sogin M L, Morrison H G, Huber J A, Mark W D, Huse S M, Neal P R, Arrieta J M, Herndl G J. Microbial diversity in the deep sea and the underexplored "rare biosphere". Proceedings of the National Academy of Sciences of the United States of America , 2006, 103 (32) : 12115–12120. DOI:10.1073/pnas.0605127103 |
| [31] | Sun L, Qiu F B, Zhang X X, Dai X, Dong X Z, Song W. Endophytic bacterial diversity in rice (Oryza sativa L.) roots estimated by 16S rDNA sequence analysis. Microbial Ecology , 2008, 55 (3) : 415–424. DOI:10.1007/s00248-007-9287-1 |
| [32] | Shannon C E, Weaver W. The Mathematical Theory of Communication. Urbana IL: University of Illinois Press, 19493–18. |
| [33] | Cottrell M T, Kirchman D L. Community composition of marine bacterioplankton determined by 16S rRNA gene clone libraries and fluorescence in situ hybridization. Applied and Environmental Microbiology , 2000, 66 (12) : 5116–5122. DOI:10.1128/AEM.66.12.5116-5122.2000 |
| [34] | Jorquera M A, Crowley D E, Marschner P, Greiner R, Teresa Fernández M, Romero D, Menezes-Blackburn D, de la Luz Mora M. Identification of beta-propeller phytase-encoding genes in culturable Paenibacillus and Bacillus spp. from the rhizosphere of pasture plants on volcanic soils. Fems Microbiology Ecology , 2011, 75 (1) : 163–172. DOI:10.1111/fem.2010.75.issue-1 |
| [35] | Leveau J H J, Uroz S, de Boer W. The bacterial genus Collimonas:mycophagy, weathering and other adaptive solutions to life in oligotrophic soil environments. Environmental Microbiology , 2010, 12 (2) : 281–292. DOI:10.1111/emi.2010.12.issue-2 |
| [36] | Xu C W, Yang M Z, Chen Y J, Chen L M, Zhang D Z, Mei L, Shi Y T, Zhang H B. Changes in non-symbiotic nitrogen-fixing bacteria inhabiting rhizosphere soils of an invasive plant Ageratina adenophora. Applied Soil Ecology , 2012, 54 : 32–38. DOI:10.1016/j.apsoil.2011.10.021 |
| [37] | Veglió F, Beolchini F, Gasbarro A. Biosorption of toxic metals:an equilibrium study using free cells of Arthrobacter sp. Process Biochemistry , 1997, 32 (2) : 99–105. DOI:10.1016/S0032-9592(96)00047-7 |
| [38] | Wakelin S A, Chu G X, Lardner R, Liang Y C, McLaughlin M. A single application of Cu to field soil has long-term effects on bacterial community structure, diversity, and soil processes. Pedobiologia , 2010, 53 (2) : 149–158. DOI:10.1016/j.pedobi.2009.09.002 |
 2016, Vol. 36
2016, Vol. 36