文章信息
- 李瑶, 席贻龙, 王爱民, 牛翔翔, 温新利, 刘桂云
- LI Yao, XI Yilong, WANG Aiming, NIU Xiangxiang, WEN Xinlin, LIU Guiyun
- 汀棠湖萼花臂尾轮虫姊妹种组成和生活史特征的时间变化
- Temporal variation in composition of Brachionus calyciflorus complex and life history traits of sibling species in Lake Tingtang
- 生态学报, 2014, 34(21): 6172-6181
- Acta Ecologica Sinica, 2014, 34(21): 6172-6181
- http://dx.doi.org/10.5846/stxb201301280179
-
文章历史
- 收稿日期:2013-1-28
- 网络出版日期:2014-3-13
轮虫是各类水体中广泛分布的一类浮游动物,在水生态系统的结构组成、物质循环和能量流动过程中具有重要的作用。由于水环境中物理﹑化学和生物因子等普遍具有随着时间的流逝或季节的更替而发生变化的特点,栖息于其中的轮虫种群也会随之发生变化[1]。为了解自然水体中轮虫种群遗传结构的时间变化,King和Zhao[2]、Gómez等[3]和江东海等[4]运用等位酶电泳技术,Ortells等[5]和董云伟等[6]运用COI基因序列测定和分析技术,项贤领等[7]应用随机扩增多态DNA(RAPD)技术,程新峰等[8]应用rDNA ITS序列测定和分析技术,研究了褶皱臂尾轮虫(B. plicatilis)和萼花臂尾轮虫等种群遗传结构的月份或季节变化。考虑到轮虫具有较短的生命周期和潜在的种群快速变化能力,King[9]首次对盖氏晶囊轮虫(Asplanchna girodi)进行每周1次的采样和克隆培养,运用等位酶电泳技术研究了其种群遗传结构的快速变化。之后,Li等[10]和温新利[11]也通过每周采样1次,运用COI基因序列测定和分析技术分别研究了北京西海和芜湖市镜湖水体中萼花臂尾轮虫种群遗传结构的快速变化。
近几年来,有关分子生物学研究和生殖隔离实验结果均表明,萼花臂尾轮虫实际上是一个种复合体[8, 12, 13, 14, 15, 16]。因此,有理由推测亚热带浅水湖泊中萼花臂尾轮虫也是一个种复合体;但种复合体结构的时间变化格局如何仍有待研究。如果种复合体内若干个姊妹种在一定时间内共存,则它们的种群内禀增长率等主要适合度参数之间可能存在无显著性差异;因为在浅水湖泊中,特定时间内较低的种复合体密度下姊妹种之间不会因为食物或空间资源等产生竞争。如果各姊妹种在各特定时间内依次从水体中消失,则可能与它们的净生殖率和种群内禀增长率等随着水温等环境因子的时间变化而发生显著的变化有关。因此,开展轮虫种复合体结构和各姊妹种生态特征的时间变化研究,将有助于理解轮虫种复合体结构的时间变化格局和机制,特别是在特定时间内姊妹种共存等的生态学机制。
本文以安徽省芜湖市汀棠湖中的萼花臂尾轮虫为对象,自2011年7月8日起,通过每周1次的轮虫采集,实验室克隆培养,DNA提取,COI基因扩增、序列测定和分析等技术研究了轮虫种复合体结构的时间变化;参照采样期间自然水温的波动范围(28—32 ℃),同时考虑到处于轻度富营养状态的汀棠湖水体中藻类和有机碎屑等轮虫食物较为丰富[17],本研究选择了在28 ℃和32 ℃等2个温度以及1.0×106、3.0×106和5.0×106 个细胞/mL等3个较高的斜生栅藻密度下研究了轮虫姊妹种生命表统计学参数的时间变化,旨在揭示亚热带浅水湖泊中萼花臂尾轮虫种复合体结构的时间变化及其生态学机制。
1 材料与方法 1.1 轮虫的采集与培养实验用萼花臂尾轮虫于2011年7月采自芜湖市汀棠湖。自7月8日起每周采集1次,直至轮虫从水体中消失为止(8月5日)。期间,分别于8日、15日、22日和29日共采得轮虫4批。本文按采得的时间顺序依次把它们定义为第1批次、第2批次、第3批次和第4批次。采样后,随机挑取带卵的萼花臂尾轮虫非混交雌体,于(25±1)℃、自然光照(光照强度约1300 lx)条件下进行克隆培养。轮虫培养液采用Gilbert配方[18],所用的饵料为HB-4培养基[19]培养的、处于指数增长期的斜生栅藻。最终被成功进行克隆培养的轮虫克隆数为59个。待轮虫繁殖至较高密度时,将每个克隆中的50—100个个体取出,经饥饿处理24 h,64 μm筛绢过滤收集,无菌水冲洗后转移至EP管中,-20 ℃处理20 min至轮虫死亡,6000 r/min离心5 min去除上清,-80 ℃保存用于分子生物学研究;剩余个体继续培养用于生命表实验研究。
1.2 DNA提取、PCR扩增、基因序列测定和分析使用WizardTM基因组DNA纯化试剂盒(Promega,USA)提取总DNA。具体方法为:将轮虫从-80 ℃中取出,加入30 μL预冷的核裂解液,56 ℃水浴1 h,室温冷却,加入10 μL预冷蛋白沉淀液,剧烈震荡2 min,15000 r/min离心10 min;吸取上清液到新离心管中,加入等量异丙醇和微量糖原混匀,15000 r/min离心10 min,沉淀经70%乙醇洗涤1次,干燥后加入20 μL TE溶解,4 ℃保存备用。
COI基因序列扩增反应在MJ Research公司生产PTC-100TM扩增仪上进行。COI基因扩增的PCR反应体系为:10×Buffer 2.5 μL,25 mmol/L MgCl2 3.3 μL,dNTP 2 μL,两条引物(10 μmol/L)各0.5 μL,DNA模板3 μL,Taq酶2 U,ddH2O补足至25 μL。COI基因扩增PCR反应程序为:94 ℃预变性5 min;94 ℃变性30 s,50℃退火30 s,72 ℃延伸1 min,循环35次;之后72 ℃充分延伸10 min,4 ℃保存。COI基因扩增引物由宝生物工程有限公司 (大连)合成,序列为HCO2198(5′-TAAACTTCAGGGTG ACCAAAAAATCA-3′)和LCO1941(5′-GGTCAA CAAATCATAAAGATATTGG-3′)[20]。PCR产物经纯化试剂盒(Tiangen)纯化后,连接到pMD 19-T载体(Takara),转化至E. coli中。挑取典型的阳性菌落至南京金斯瑞生物科技有限公司测序,测序使用ABI 3730测序仪。
采用CLUSTAL X(1.8)软件[21]进行序列对位排列,并辅以人工校对;用DNASTAR软件计算两两序列的差异百分比。
系统发生树的构建方法与项贤领等[14]基本相同。
1.3 生命表实验和相关参数的定义与计算根据COI序列差异百分比和系统发生关系分析结果,分别以第1、2和3批次中的姊妹种T1仅有的8个、5个和1个克隆,第3批次中的姊妹种T2仅有的3个克隆,加之从第1、2和4批次中随机选取的姊妹种T2各10个克隆(共47个克隆)用于生命表统计学参数研究。实验设28 ℃和32 ℃等2个温度以及1.0×106、3.0×106和5.0×106个细胞/mL等3个斜生栅藻密度。实验前,将47个轮虫克隆分别置于6个温度-食物密度组合条件下进行为期1周的预培养,预培养在光照培养箱中进行,光照强度约1300 lx。预培养过程中,每12 h悬浮1次沉积于试管底部的藻类食物;每24 h更换轮虫培养液并投喂饵料1次,同时除去一部分个体使轮虫种群始终处于指数增长期。
实验时,从预培养1周后的各轮虫克隆中吸取若干个带卵的非混交雌体,分别置于和预培养条件相同的玻璃杯中进行培养;期间,每隔4 h观察1次,由此获得若干个龄长小于4 h的轮虫幼体用于生命表实验。实验在8 mL的玻璃杯中进行,轮虫培养液体积为5 mL。每个玻璃杯中培养的轮虫幼体为10个,分别来自10个轮虫克隆所产的龄长小于4 h的幼体(第1、2和3批次中的姊妹种T1来自仅有的8个、5个和1个克隆,第3批次中的姊妹种T2来自仅有的3个克隆);实验设5个重复。实验条件与预培养相同。实验过程中,每隔8 h观察1次,计数各玻璃杯中轮虫母体的存活数和孵化出的幼体数,并移去死亡个体;将孵化出的幼体转移至另一个玻璃杯中在同样条件下继续培养,待其携卵后确定雌体类型;观察的同时用微吸管悬浮沉于杯底的藻细胞;每隔24 h更换培养器皿和培养液并投喂食物1次。实验至全部个体死亡时为止。
生命表统计学参数的定义和计算方法与刘宁等[22]基本相同。
1.4 数据处理和分析方法采用SPSS 16.0统计分析软件对生命表统计学参数进行统计分析。对所得的各生活史参数进行正态分布检验后,对符合正态分布的数据进行方差分析。运用三因素方差分析法分析温度、食物密度、批次及其交互作用对轮虫各姊妹种各生命表统计学参数的影响,以及温度、食物密度、姊妹种及其交互作用对轮虫各批次各生命表统计学参数的影响,采用多重比较(SNK-q检验法)分析2温度间、3食物密度间、3或4批次间轮虫各姊妹种各生活史参数的差异显著性,以及各批次2轮虫姊妹种间各生活史参数的差异显著性。
2 结果与分析 2.1 COI基因序列特点和姊妹种组成扩增所得COI基因部分序列长度为661 bp,其中变异位点、多态位点和简约信息位点分别为131个、40个和91个;59条序列共定义38个单倍型,其中共享单倍型4个(表 1,表 2)。
| 采样批次 Collection batch | 采样时间 Collection date | 种群代号 Population code | 克隆数 n |
| 1 | 07-08 | YA | 22 |
| 2 | 07-15 | LB | 16 |
| 3 | 07-22 | LC | 4 |
| 4 | 07-29 | LD | 17 |
| 共享单倍型 Shared haplotypes | 克隆 Clones |
| SH1 | YA22,YA10,YA20 |
| SH2 | YA11,LD34 |
| SH3 | YA29,LB18,LB21,LB44 |
| SH4 | YA26,YA19,YA6,YA31,YA14,YA21,LB5,LB41,LB35,LC1,LC2,LC11,LD4,LD9,LD20,LD21 |
运用贝叶斯法、最大似然法、最大简约法和邻接法构建的系统发生树的拓扑结构基本一致(图 1)。38个单倍型以较高置信度聚合为2个支系:支系Ⅰ和支系Ⅱ。
所有38个单倍型间序列差异百分比为0—15.6%,平均为8.27%。支系Ⅰ和支系Ⅱ内部COI基因部分序列差异百分比分别为0—1.2%和0—1.1%,支系Ⅰ和支系Ⅱ间的序列差异百分比为13.9%—15.6%。根据李化炳等[13]和Xiang等[15, 23]对芜湖市几个水体中萼花臂尾轮虫姊妹种间的交配实验和COI基因部分序列分析结果,本研究中的支系Ⅰ和支系Ⅱ应属不同的姊妹种,分别命名为姊妹种T1和姊妹种T2。

|
| 图 1 基于萼花臂尾轮虫59条COI基因部分序列构建的系统发生树 Fig. 1 Phylogenetic trees based on partial sequences of 59 COI genes of B. calyciflorus |
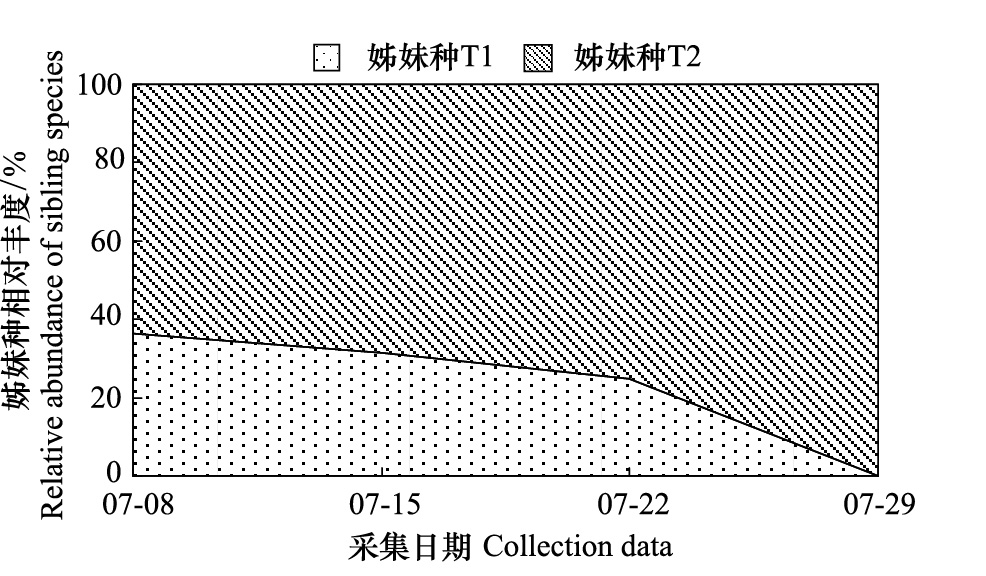
汀棠湖中,萼花臂尾轮虫种复合体内两姊妹种的相对丰度随着时间的推移而呈现快速变化的特点。姊妹种T1的相对丰度由第1批次向第3批次快速降低,直至第4批次从水体中消失;与此相反,姊妹种T2的相对丰度却随着时间的推移而逐渐升高(图 2)。
|
| 图 2 汀棠湖萼花臂尾轮虫两姊妹种的相对丰度 Fig. 2 Relative abundance of the two sibling species in B. calyciflorus complex from Lake Tingtang |
汀棠湖中,萼花臂尾轮虫两姊妹种的遗传多样性并不随采集时间的推移而呈现出规律性的变化(表 3)。
|
种群代号 Population code | 姊妹种T1 sibling species T1 | 姊妹种T2 sibling species T2 | ||||
| n | h | p | n | h | p | |
| YA | 8 | 0.893±0.111 | 0.00351±0.00090 | 14 | 0.835±0.101 | 0.00271±0.00066 |
| LB | 5 | 1.000±0.126 | 0.00787±0.00156 | 11 | 0.891±0.074 | 0.00374± 0.00071 |
| LC | 1 | - | - | 3 | 0.000±0.000 | 0.0000±0.00000 |
| LD | 0 | - | - | 17 | 0.956±0.044 | 0.00372±0.00069 |
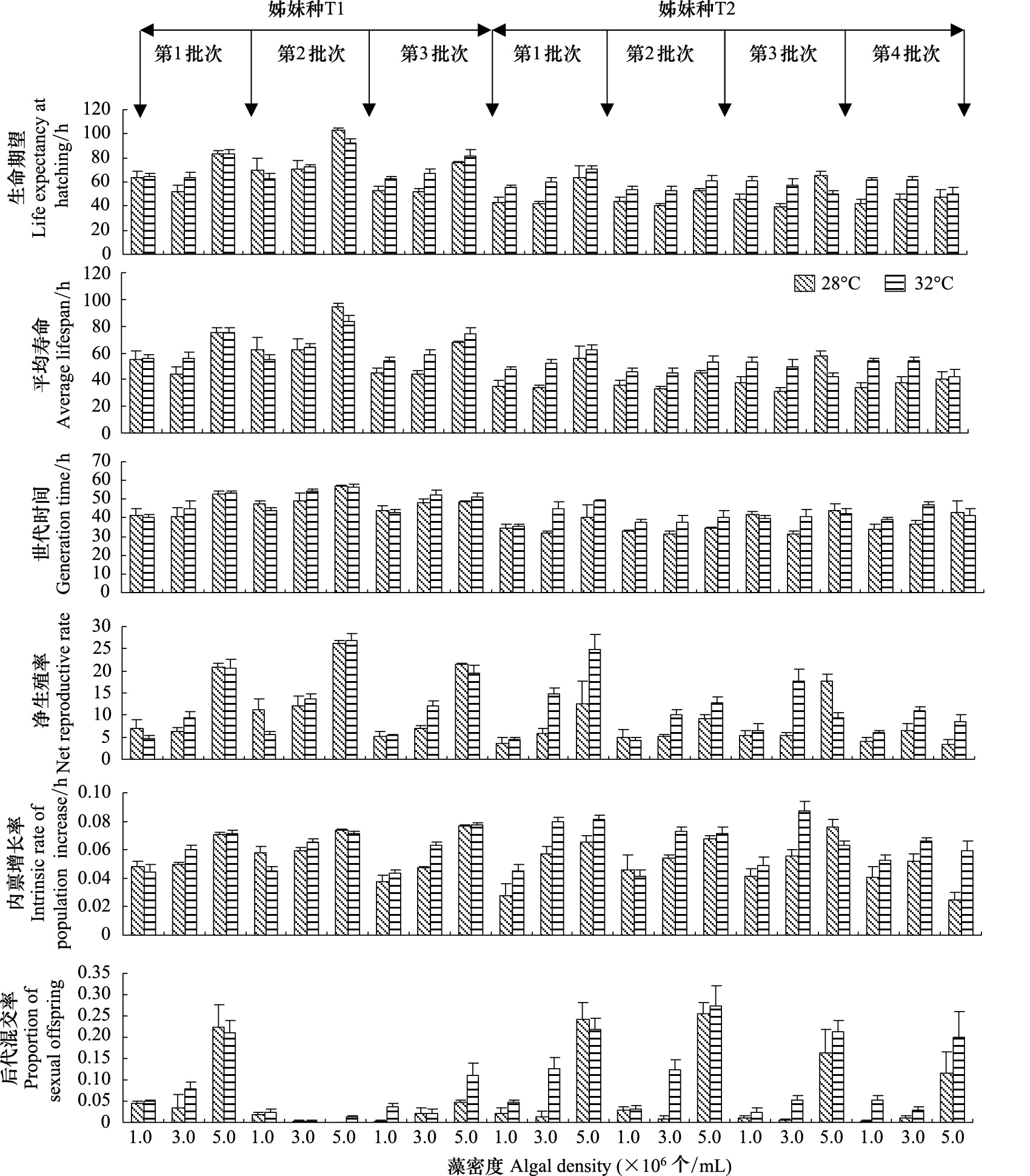
基于2温度和3食物密度下、各批次采自汀棠湖中的萼花臂尾轮虫2姊妹种的存活率和繁殖率算得的各生命表统计学参数列于图 3。
|
| 图 3 2温度和3食物密度下各批次采集的萼花臂尾轮虫2姊妹种出生时的生命期望、平均寿命、世代时间、净生殖率、内禀增长率和后代混交率 (均数±标准误) Fig. 3 Life expectancy at hatching,average lifespan,generation time,net reproductive rate,intrinsic rate of population increase and proportion of sexual offspring of two sibling species in B. calyciflorus complex collected at four batches from Lake Tingtang and cultured at two temperatures and three food levels (Mean±SE) |
三因素方差分析表明,温度对轮虫姊妹种T1各生命表统计学参数均无显著的影响(P>0.05),但对轮虫姊妹种T2各生命表统计学参数均有极显著的影响(P<0.01);食物密度对2姊妹种各生命表统计学参数均有极显著的影响(P<0.01);批次对姊妹种T1各生命表统计学参数均有极显著的影响(P<0.01),对姊妹种T2的世代时间、净生殖率、内禀增长率和后代混交率有显著的影响(P<0.05)(表 4)。
|
因子
Factor | 生命期望
Life expectancy at hatching | 平均寿命
Average lifespan | 世代时间
Generation time | 净生殖率
Net reproductive rate | 内禀增长率
Intrinsic rate of population increase | 后代混交率
Proportion of sexual offspring |
| ** P<0.01,* P<0.05,P>0.05 | ||||||
| 姊妹种T1 Sibling species T1 | ||||||
| 温度Temperature (A) | - | - | - | - | - | - |
| 食物密度Food level (B) | ** | ** | ** | ** | ** | ** |
| 批次Batch (C) | ** | ** | ** | ** | ** | ** |
| A×B | - | - | - | ** | ** | - |
| B×C | - | - | * | - | ** | ** |
| A×C | * | * | - | - | ** | - |
| A×B×C | - | - | - | - | - | - |
| 姊妹种T2 Sibling species T2 | ||||||
| 温度Temperature (A) | ** | ** | ** | ** | ** | ** |
| 食物密度Food level (B) | ** | ** | ** | ** | ** | ** |
| 批次Batch (C) | - | - | * | ** | ** | ** |
| A×B | ** | ** | * | ** | * | - |
| B×C | ** | ** | - | ** | ** | - |
| A×C | - | - | - | * | - | - |
| A×B×C | - | - | - | ** | ** | - |
轮虫各生命表统计学参数对升高的温度和食物密度以及增加的采集批次的反应在2姊妹种间存在着差异。姊妹种T1的所有生命表统计学参数均不受温度的显著影响(P>0.05),而姊妹种T2的所有生命表统计学参数均随着温度的升高而显著地增大(P<0.05)。
轮虫2姊妹种的平均寿命、出生时的生命期望和后代混交率对升高的食物密度的反应相似,均表现为1.0×106个细胞/mL和3.0×106个细胞/mL食物密度下较短或较低,5.0×106个细胞/mL食物密度下较长或较高。姊妹种T1的世代时间、净生殖率和种群内禀增长率以及姊妹种T2的净生殖率均随着食物密度的升高而延长或增大;而姊妹种T2的世代时间在1.0 ×106和3.0×106个细胞/mL食物密度下较短,5.0×106个细胞/mL食物密度下较长;姊妹种T2的种群内禀增长率在1.0×106个细胞/mL较低,在3.0×106和5.0×106个细胞/mL食物密度下较高。
轮虫姊妹种T1的后代混交率以第1批次最高,第2批次最低;其它所有生命表统计学参数均以第2批次较大,第1和第3批次较小。姊妹种T2的平均寿命和出生时的生命期望不受采集批次的显著影响(P>0.05);世代时间以第2批次显著长于第3和第4批次,但三者均与第1批次间无显著的差异;净生殖率以第1和第3批次较高,第2和第4批次较低;种群内禀增长率以第1—3批次较高,第4批次较低;后代混交率均以第1和第2批次较高,第3和第4批次较低。
分别对前3个批次轮虫各生命表统计学参数所作的三因素方差分析结果表明,姊妹种对各个批次轮虫的平均寿命、生命期望和世代时间均有显著的影响(P<0.05);对第2批次轮虫的净生殖率有显著的影响(P<0.05),对第2和第3批次轮虫的后代混交率均有显著的影响(P<0.05)(表 5)。
第1、2和3批次中,姊妹种T1的平均寿命、出生时的生命期望和世代时间均显著长于姊妹种T2;第2批次中,姊妹种T1的净生殖率显著高于姊妹种T2,后代混交率则相反;第3批次中,姊妹种T1的后代混交率显著低于姊妹种T2。
3 讨论 3.1 轮虫姊妹种的甄别COI基因序列特别适用于轮虫种类识别(包括形态上难以区分甚至不可能区分的、同域性分布的姊妹种)、种内变异和系统地理学等研究[13, 15, 24, 25]。其它分子标记,如16S rRNA序列和ITS序列也曾被用于单巢目轮虫的系统发生分析和姊妹种识别研究[12, 26, 27, 28, 29];但它们与COI基因序列相比,种间的序列分化程度较低。应用ITS序列甄别同域性分布的萼花臂尾轮虫姊妹种时,无法对个别轮虫克隆的姊妹种归属进行准确的判断[13]。因此,本研究以COI基因序列为标记,对同一水体中分布的萼花臂尾轮虫姊妹种进行了甄别。
| 因子Factor | 生命期望 e0 | 平均寿命 LS | 世代时间 T | 净生殖率 R0 | 内禀增长率 rm | 后代混交率 PS |
| ** P < 0.01,* P < 0.05,P > 0.05 | ||||||
| 第1批次 The first batch | ||||||
| 温度Temperature (A) | ** | ** | * | ** | ** | - |
| 食物密度Food level (B) | ** | ** | ** | ** | ** | ** |
| 姊妹种Sibling species (C) | ** | ** | ** | - | - | - |
| A×B | - | - | - | * | ** | * |
| B×C | - | - | - | - | ** | - |
| A×C | - | - | - | ** | ** | - |
| A×B×C | - | - | - | - | - | - |
| 第2批次The second batch | ||||||
| 温度Temperature (A) | - | - | * | - | - | * |
| 食物密度Food level (B) | ** | ** | ** | ** | ** | ** |
| 姊妹种Sibling species (C) | ** | ** | ** | ** | - | ** |
| A×B | - | - | - | ** | ** | - |
| B×C | ** | ** | * | ** | - | ** |
| A×C | ** | ** | * | * | * | * |
| A×B×C | - | - | - | - | - | * |
| 第3批次The third batch | ||||||
| 温度Temperature (A) | ** | ** | - | - | ** | ** |
| 食物密度Food level (B) | ** | ** | * | ** | ** | ** |
| 姊妹种Sibling species (C) | ** | ** | ** | - | - | ** |
| A×B | ** | ** | * | ** | ** | ** |
| B×C | ** | ** | ** | ** | ** | ** |
| A×C | - | - | - | - | - | - |
| A×B×C | * | * | - | ** | - | - |
已有研究结果表明,萼花臂尾轮虫姊妹种之间的COI基因序列差异为7.2%—26.8%[12, 13, 15, 23],褶皱臂尾轮虫姊妹种(B. plicatilis、B. ibericus和B. rotundiformis)之间的COI基因序列差异为22.8%—25.6%,螺形龟甲轮虫(Keratella cochlearis)姊妹种之间的COI基因序列差异为4.4%[26]。本研究中,支系Ⅰ和支系Ⅱ间的序列差异百分比为13.9%—15.6%。根据李化炳等[13]、Xiang等[15, 23]对芜湖市几个水体中萼花臂尾轮虫姊妹种间的交配实验和COI基因部分序列分析结果,支系Ⅰ和支系Ⅱ应属不同的姊妹种。
3.2 轮虫姊妹种组成和生态特征的时间变化格局秋季的北京西海中,萼花臂尾轮虫姊妹种A和B仅在第1批次的采集中共存;相对丰度较低的姊妹种B在第2批次的采集中即从水体中消失[10]。冬春季(2008年12月30日—2009年4月5日)的芜湖市镜湖中,萼花臂尾轮虫两姊妹种长时间共存[11]。西班牙地中海海滨池塘中,褶皱臂尾轮虫种复合体由几个姊妹种组成,部分姊妹种的分布在时间上重叠(共存)[3, 5]。本研究中,萼花臂尾轮虫种复合体内两姊妹种的相对丰度随着时间的推移而呈现快速变化的特点。姊妹种T1的相对丰度由第1批次向第3批次快速降低,至第4批次从水体中消失;与此相反,姊妹种T2的相对丰度却随着时间的推移而逐渐升高,至8月5日从水体中消失。可见,种复合体结构的时间变化格局可能因水体和轮虫种类的不同而异,但同一水体中的姊妹种共存可能是一个普遍现象。
汀棠湖中,萼花臂尾轮虫不仅在姊妹种组成上具有快速变化的特点,姊妹种T1各生命表统计学参数以及姊妹种T2的世代时间、净生殖率、内禀增长率和后代混交率等也均具有明显的快速变化格局。由于轮虫各姊妹种均由若干个基因型不同的克隆组成,各姊妹种种群遗传结构也随着时间的推移而发生显著的变化,因此,本研究所揭示的轮虫生活史等生态特征的快速变化格局主要由遗传因素决定。
3.3 姊妹种组成快速变化的生态学机制探讨从种群生态学和进化生态学等的角度来看,姊妹种共存的前提是各种群至少应在竞争能力和个体适合度等方面相同,或具有明显的生态位分化,或自然水环境的多变不足以形成稳定的环境而导致种群间的竞争。相反,随着季节的变化,共存的姊妹种的相继消失则意味着其在竞争能力或个体适合度等方面可能处于劣势。自然水体中褶皱臂尾轮虫种复合体可在短时间内达到较高的密度[30, 31],据此推测其姊妹种之间可能存在着资源竞争[32]。尽管实验室研究发现B. plicatilis、B. ibericus和B. rotundiformis等3个个体较小但存在形态差异的姊妹种之间可产生资源竞争[33],对温度和盐度的适应性、在资源利用和防捕食能力等方面的差异也解释了种间竞争的结局[33, 34, 35];但实验室研究和野外调查发现生态特化(姊妹种的生态位分化)是其共存的主要原因[3, 5]。同样,B. plicatilis和B. manjavacas等形态和大小高度相似的姊妹种共存的原因,在于其对升高的盐度的不同反应造成了它们的生态位分化,导致了它们的共存[36]。
汀棠湖中,萼花臂尾轮虫种复合体的密度在7月份较低(<20 个/L)[11];如此低的密度下,两姊妹种之间应不会因为食物或空间资源等产生竞争;两姊妹种在种群内禀增长率等主要适合度参数之间的无显著性差异是它们能够共存于同一水体中的另一主要原因。而姊妹种T1和姊妹种T2在7月29日和8月5日依次从水体中消失则与它们在1周前净生殖率和种群内禀增长率显著降低有关。消失时间上的差异可能在于姊妹种T1的所有生命表统计学参数均不受温度的显著影响,而姊妹种T2的所有生命表统计学参数均随着温度的升高而显著地增大。
| [1] | King C E, Serra M. Seasonal variation as a determinant of population structure in rotifers reproducing by cyclical parthenogenesis. Hydrobiologia, 1998, 387-388: 361-372. |
| [2] | King C E, Zhao Y G. Coexistence of rotifer (Branchionus plicatilis) clones in Soda Lake, Nevada. Hydrobiologia, 1987, 147(1): 57-64. |
| [3] | Gómez A, Temprano M, Serra M. Ecological genetics of a cyclical parthenogen in temporary habitats. Journal of Evolutionary Biology, 1995, 8(5): 601-622. |
| [4] | Jiang D H, Xi Y L, Liu S G, Zhang L, Dong L L. Allozyme analysis on Brachionus calyciflorus (Rotifera) population in Lake Jinghu and seasonal variation of their reproductive parameters. Acta Hydrobiologica Sinica, 32(6): 908-915. |
| [5] | Ortells R, Gómez A, Serra M. Coexistence of cryptic rotifer species: ecological and genetic characterization of Brachionus plicatilis. Freshwater Biology, 2003, 48(12): 2194-2202. |
| [6] | Dong Y W, Niu C J. Sequence variability of mitochondrial COI region and population genetic structure of rotifer Brachionus calyciflorus. Oceanologia et Limnologia Sinica, 2004, 35(5): 473-480. |
| [7] | Xiang X L, Xi Y L, Hu H Y. Seasonal changes in the genetic diversity of Brachionus calyciflorus population in Lake Jinghu. Acta Ecologica Sinica, 2007, 27(6): 2443-2448. |
| [8] | Cheng X F, Xi Y L, Li H B. Seasonal changes in the genetic structure of a Brachionus calyciflorus population in Lake Liantang based on ITS sequences. Acta Zoologica Sinica, 2008, 54: 245- 255. |
| [9] | King C E. Genetics of reproduction, variation and adaptation in rotifers. Archiv für Hydrobiologie Beiheft, 1977, 8: 187-201. |
| [10] | Li L, Niu C J, Ma R. Rapid temporal succession identified by COI of the rotifer Brachionus calyciflorus Pallas in Xihai Pond, Beijing, China, in relation to ecological traits. Journal of Plankton Research, 2010, 32(6): 951-959. |
| [11] | Wen X L. Population Dynamics and Regulation Mechanisms of Brachionus calyciflorus and Brachionus angularis (Rotifera) in Two Shallow Eutrophic Lakes [D]. Anhui: Anhui Normal University, 2011. |
| [12] | Gilbert J J, Walsh E J. Brachionus calyciflorus is a species complex: mating behavior and genetic differentiation among four geographically isolated strains. Hydrobiologia, 2005, 546(1): 257-265. |
| [13] | Li H B, Xi Y L, Cheng X F, Xiang X L, Hu C B, Tao L X. Sympatric speciation in rotifers: evidence from molecular phylogenetic relationships and reproductive isolation among Brachionus calyciflorus clones. Acta Zoologica Sinica, 2008, 54(2): 256-264. |
| [14] | Xiang X L, Xi Y L, Wen X L, Zhang J Y, Ma Q. Spatial patterns of genetic differentiation in Brachionus calyciflorus species complex. Zoological Research, 2010, 31(3): 205-220. |
| [15] | Xiang X L, Xi Y L, Wen X L, Zhang G, Wang J X, Hu K. Genetic differentiation and phylogeographical structure of the Brachionus calyciflorus complex in eastern China. Molecular Ecology, 2011, 20(14): 3027-3044. |
| [16] | Xiang X L, Xi Y L, Wen X L, Zhang G, Wang J X, Hu K. Patterns and processes in the genetic differentiation of the Brachionus calyciflorus complex, a passively dispersing freshwater zooplankton. Molecular Phylogenetics and Evolution, 2011, 59(2): 386-398. |
| [17] | Wen X L, Xi Y L, Qian F P, Zhang G, Xiang X L. Comparative analysis of rotifer community structure in five subtropical shallow lakes in east China: role of physical and chemical conditions. Hydrobiologia, 2011, 661(1): 303-316. |
| [18] | Gilbert J J. Mictic female production in the rotifer Brachionus calyciflorus. Journal of Experimental Zoology, 1963, 153(2): 113-124. |
| [19] | Zhang Z S, Huang X F. Methods for Studying on Freshwater Plankton. Beijing: Science Press, 1991: 410-411. |
| [20] | Folmer O, Black M, Hoeh W, Lutz R, Vrijenhoek R. DNA primers for amplification of mitochondrial cytochrome c oxidase subunit I from diverse metazoan invertebrates. Molecular Marine Biology and Biotechnology, 1994, 3(5): 294-299. |
| [21] | Thompson J D, Gibson T J, Plewniak F, Jeanmougin F, Higgins D G. The clustal_x windows interface: flexible strategies for multiple sequence alignment aided by quality analyses tools. Nucleic Acids Research, 1997, 25(24): 4876-4882. |
| [22] | Liu N, Xi Y L, Shen P, Yang S, Song X, Sun T B. Effects of lead concentration and algal density on life table demography of Moina macrocopa. Acta Ecologica Sinica, 2010, 30(18): 4866-4874. |
| [23] | Xiang X L, Xi Y L, Wen X L, Zhang J Y, Ma Q. Spatial patterns of genetic differentiation in Brachionus calyciflorus species complex collected from East China in summer. Hydrobiologia, 2010, 638(1): 67-83. |
| [24] | Birky C W Jr, Wolf C, Maughan H, Herbertson L, Henry E. Speciation and selection without sex. Hydrobiologia, 2005, 546(1): 29-45. |
| [25] | Gómez A. Molecular ecology of rotifers: from population differentiation to speciation. Hydrobiology, 2005, 546(1): 83-99. |
| [26] | Derry A M, Hebert P D N, Prepas E E. Evolution of rotifers in saline and subsaline lakes: a molecular phylogenetic approach. Limnology and Oceanography, 2003, 48(2): 675-685. |
| [27] | Papakostas S, Triantafyllidis A, Kappas I, Abatzopoulos T J. The utility of the 16S gene in investigating cryptic speciation within the Brachionus plicatilis species complex. Marine Biology, 2005, 147(5): 1129-1139. |
| [28] | Gómez A, Serra M, Carvalho G R, Lunt D H. Speciation in ancient cryptic species complexes: evidence from the molecular phylogeny of Brachionus plicatilis (Rotifera). Evolution, 2002, 56(7): 1431-1444. |
| [29] | Suatoni E, Vicario S, Rice S, Snell T, Caccone A. An analysis of species boundaries and biogeographic patterns in a cryptic species complex: the rotifer Brachionus plicatilis. Molecular Phylogenetics and Evolution, 2006, 41(1): 86-98. |
| [30] | Carmona M J, Gómez A, Serra M. Mictic patterns of the rotifer Brachionus plicatilis Müller in small ponds. Hydrobiology, 1995, 109: 365-371. |
| [31] | Carmona M J, Dimas-Flores N, Garcia-Roger E M, Serra M. Selection of low investment in sex in a cyclically parthenogenetic rotifer. Journal of Evolutionary Biology, 2009, 22(10): 1975-1983. |
| [32] | Cordova S E, Giffin J, Kirk K L. Food limitation of planktonic rotifers: field experiments in two mountain ponds. Freshwater Biology, 2001, 46(11): 1519-1527. |
| [33] | Ciros-Pérez J, Carmona M J, Lapesa S, Serra M. Predation as a factor mediating resource competition among rotifer sibling species. Limnology and Oceanography, 2004, 49(1): 40-50. |
| [34] | Gómez A, Carmona M J, Serra M. Ecological factors affecting gene flow in the Brachionus plicatilis complex (Rotifera). Oecologia, 1997, 111(3): 350-356. |
| [35] | Ciros-Pérez J, Carmona M J, Serra M. Resource competition between sympatric sibling rotifer species. Limnology and Oceanography, 2001, 46(6): 1511-1523. |
| [36] | Montero-Pau J, Ramos-Rodríguez E, Serra M, Gómez A, Steinke D. Long-term coexistence of rotifer cryptic species. PLoS ONE, 2011, 6(6): e21530. |
| [4] | 江东海, 席贻龙, 刘胜国, 张雷, 董丽丽. 镜湖萼花臂尾轮虫种群等位酶分析和生殖参数的季节变化. 水生生物学报, 32(6): 908-915. |
| [6] | 董云伟, 牛翠娟. 萼花臂尾轮虫 (Brachionus calyciflorus) COI 基因序列变异及种群遗传结构分析. 海洋与湖沼, 2004, 35(5): 473-480. |
| [7] | 项贤领, 席贻龙, 胡好远. 镜湖萼花臂尾轮虫种群遗传多样性的季节变化. 生态学报, 2007, 27(6): 2443-2448. |
| [8] | 程新峰, 席贻龙, 李化炳. 基于rDNA ITS序列分析莲塘湖萼花臂尾轮虫种群遗传结构的季节变化. 动物学报, 2008, 54(2): 245-255. |
| [11] | 温新利. 浅水富营养湖泊中两种臂尾轮虫的种群变动和机制研究 [D]. 安徽: 安徽师范大学, 2011. |
| [13] | 李化炳, 席贻龙, 程新峰, 项贤领, 胡存兵, 陶李祥. 轮虫同域性物种形成: 来自萼花臂尾轮虫克隆间的分子系统发育关系和生殖隔离证据. 动物学报, 2008, 54(2): 256-264. |
| [14] | 项贤领, 席贻龙, 温新利, 张晋艳, 马芹. 萼花臂尾轮虫种复合体遗传分化的空间格局. 动物学研究, 2010, 31(3): 205-220. |
| [19] | 章宗涉, 黄祥飞. 淡水浮游生物研究方法. 北京: 科学出版社, 1991: 410-411. |
| [22] | 刘宁, 席贻龙, 沈鹏, 杨胜, 宋鑫, 孙天宝. Pb2+浓度和藻类食物密度对多刺裸腹溞生命表统计学参数的影响. 生态学报, 2010, 30(18): 4866-4874. |
 2014, Vol. 34
2014, Vol. 34