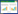文章信息
- 冯慧, 黄原, 任轶, 冯成利, 刘晓农
- FENG Hui, HUANG Yuan, REN Yi, FENG Chengli, LIU Xiaonong
- 陕西省林麝mtDNA D-loop区序列结构和种群遗传多样性
- Structure of the mitochondrial DNA D-Loop region and genetic diversity of Moschus berezovskii in Shaanxi Province
- 生态学报, 2013, 34(20): 5887-5895
- Acta Ecologica Sinica, 2013, 34(20): 5887-5895
- http://dx.doi.org/10.5846/stxb201305221148
-
文章历史
- 收稿日期:2013-5-22
- 网络收稿日期:2014-3-11
2. 陕西师范大学, 西安 710062
2. Shaanxi Normal University, Xi'an 710062, China
林麝(Moschus berezovskii)是哺乳纲偶蹄目鹿科麝属的一种动物[1, 2],又名香獐、獐子、山驴、林獐、麝鹿等。因雄麝在脐部和生殖器之间有香囊,能分泌和贮存麝香,故得名香獐,是珍贵的野生药用资源动物。数据显示,世界上70%的麝香和与麝香相关的产物都来自中国[3, 4]。是国家一级保护动物[5],曾广泛分布于中国,由于非法盗猎、栖息地破碎化等影响[6, 7, 8],野生林麝仅在陕西的凤县、陇县、镇平、留坝等地呈零星状分布[9],数量由8万只锐减到4000 只左右[10],已濒临灭绝[11]。因此研究林麝遗传多样性对林麝资源的保护和开发利用意义重大。 线粒体DNA(Mitochondrial DNA,mtDNA)是核外遗传物质,因为具有以母系遗传方式遗传,其结构简单、稳定,世代间没有基因重组且进化速度较快,能更直观保存群体突变发生的特点,被广泛应用于种群遗传多样性研究[12]。mtDNA D-环(D-loop)是线粒体基因组的非编码区,也叫控制区,富含A、T碱基,属于遗传高变区,进化速度比其他mtDNA区域快,多态性丰富[13],由于 mtDNA D-loop 区的独特特性,经常被应用到野生动物群体遗传多样性检测、群体遗传结构分析、亚种与种群分化等方面研究中。Hiendleder 等对欧、亚绵羊品种的控制区进行了遗传多样性分析,将欧、亚群体分为两大母系起源[14]。张涛等用mtDAN D-Loop区序列研究宁强矮马的遗传多样性,结果显示,虽然宁强矮马群体内存在一定程度的近交现象,但还是存在较为丰富的多态性[15]。林麝mtDNA的研究也已经展开,彭红元研究了林麝mtDNA序列,结果显示林麝与鹿科动物有更近的亲缘关系[16]。H.Peng等利用林麝mtDNA部分序列对比了四川3 个人工养殖种群的遗传多样性[17]。因此,本研究对秦岭3 个地区69 个林麝个体的mtDNA D-loop部分序列进行测序,并分析其遗传多样性,从而为该种群遗传多样性和保护生物学的研究提供科学资料。
1 材料与方法 1.1 材料来源从凤县采集野生林麝毛发以及病死林麝肌肉组织39 个个体样品;凤县3 个养殖场采集14 个个体毛发样品;留坝和陇县野生林麝肌肉样品分别为9 个和7 个。肌肉样品于无水乙醇中固定,带回实验室保存于-20 ℃冰箱。 用于毛发DNA提取的Chelex-100购自Bio-Rad公司,引物由上海生工生物工程技术服务有限公司合成。
1.2 方法 1.2.1 mtDNA的提取毛发mtDNA的提取参照周月琴[18]等的方法进行。所用玻璃器皿和塑料耗材均经过高温高压灭菌处理。另外,由于所用实验材料有些为在地上拾取的陈旧毛发,其遗传物质可能已有部分降解,提取过程中实验者本人及其他生物极可能对其造成外源污染。因此,在实验中设定了空白提取对照,即设定除不加实验样品外其它所有提取步骤都与样品处理完全一致的平行对照实验。野生林麝毛发经微卫星鉴定个体后使用。 肌肉组织DNA提取方法参照Sambrook和蔡振媛等用蛋白酶K和苯酚从哺乳动物细胞中分离高分子质量DNA的方法[19, 20]提取总DNA。
1.2.2 PCR扩增及其产物的测定引物为L: 5′-CAACTAACCTCCCTAAGACTTCAAG-3′; H:5′-CCAAATGTATGACAGCACAGTTATG-3′。PCR反应总体积为50 μL,其中10×PCR Buffer 5.0 μL,dNTP (200 μmol/L) 1.0 μL,DNA模板2 μL,上下游引物(0.2 μmol) 各2 μL,Taq酶(5 U/μL) 0.4 μL,超纯灭菌水37.6 μL。PCR 反应体系在95 ℃预变性1 min,94 ℃预变性4 min,94 ℃变性30 s,56 ℃退火45 s,68 ℃延伸1 min,共35循环,最后一循环保温10 min,4 ℃ 保存备用。利用未加模板DNA的反应液作为空白对照,以检查是否有污染存在。PCR 扩增产物采用1.0%琼脂糖凝胶电泳检测其片段大小与浓度,于-20 ℃保存。产物送至上海英骏生物技术有限公司进行纯化,在ABI3730 型自动测序仪上双向测序。
1.2.3 DNA序列数据处理以 GenBank 已发表的林麝序列AY835375.1为参考序列,将所有序列使用Clustalx1.81软件进行整合对比[21],Seaview 软件检查比对结果并手动校正[22]并去掉残留的引物序列。利用 DNASP4.10[23]软件统计种群核苷酸多样性(Pi)、序列的单倍型数(h)、单倍型多样度(Hd)、平均核苷酸差异数(K)等。用Mega5.05[24]软件计算碱基组成和差异和个体间遗传距离。用MEGA5.0软件计算群体间和群体内Kimura 2-parameter模型的遗传距离;分析碱基组成及核苷酸位点的替换数;用1000次Bootstrap重复分析,构建Neighbour-joining系统进化树。用 Network[25]软件建立网状亲缘关系图,分析各群体单倍型之间的进化关系。
2 结果 2.1 林麝mtDNA D-Loop区PCR扩增结果林麝mtDNA D-Loop 扩增片段长度为635—637 bp,结果见图 1。

|
| 图 1 林麝D-Loop区部分序列扩增电泳图 Fig. 1 PCR result of mtDNA D-loop partial sequences in Moschus berezovskii |
通过PCR获得69 个林麝mtDNA D-Loop 区 DNA 片段,经过双向测序、比对校正后除去重复区得到632 bp的序列,序列中A、T、G和C 4种核苷酸的平均比例分别为32.2%、31.0%、14.4%和22.4%,A+T含量为63.2%,G + C含量为36.8%。A+T含量高于G+C含量,说明林麝线粒体 DNAD-loop区部分序列富含A+T;表现出碱基组成的偏倚性。与NCBI公布的林麝D-Loop序列(AY835375.1)对比发现有32 个单倍型(表 1),171 个多样性位点,73 个单一变异位点,98 个简约信息位点,占分析位点总数的27.05%。
| 单倍型Haplo-type | 群体号Population number | 单倍型Haplo-type | 群体号Population number | ||||||
| 凤县野生 | 凤县养殖场 | 留坝 | 陇县 | 凤县野生 | 凤县养殖场 | 留坝 | 陇县 | ||
| Hap1 | 2 | 0 | 4 | 0 | Hap17 | 1 | 0 | 0 | 0 |
| Hap2 | 1 | 0 | 0 | 2 | Hap18 | 5 | 1 | 0 | 0 |
| Hap3 | 11 | 3 | 1 | 0 | Hap19 | 0 | 0 | 1 | 0 |
| Hap4 | 0 | 0 | 0 | 1 | Hap20 | 1 | 0 | 0 | 0 |
| Hap5 | 1 | 0 | 0 | 0 | Hap21 | 1 | 0 | 0 | 0 |
| Hap6 | 5 | 0 | 0 | 2 | Hap22 | 0 | 1 | 0 | 0 |
| Hap7 | 0 | 0 | 0 | 1 | Hap23 | 1 | 0 | 0 | 0 |
| Hap8 | 1 | 0 | 0 | 0 | Hap24 | 0 | 0 | 1 | 0 |
| Hap9 | 1 | 0 | 0 | 0 | Hap25 | 0 | 1 | 0 | 0 |
| Hap10 | 1 | 0 | 0 | 0 | Hap26 | 0 | 1 | 0 | 0 |
| Hap11 | 1 | 0 | 0 | 0 | Hap27 | 0 | 0 | 1 | 0 |
| Hap12 | 1 | 1 | 0 | 0 | Hap28 | 1 | 0 | 0 | 0 |
| Hap13 | 0 | 1 | 1 | 0 | Hap29 | 0 | 0 | 0 | 1 |
| Hap14 | 0 | 1 | 0 | 0 | Hap30 | 0 | 1 | 0 | 0 |
| Hap15 | 2 | 2 | 0 | 0 | Hap31 | 1 | 0 | 0 | 0 |
| Hap16 | 0 | 1 | 0 | 0 | Hap32 | 1 | 0 | 0 | 0 |
利用DNAsp软件计算了林麝69个个体mtDNA D-loop序列的遗传多样性指数(表 2),单倍型多样度(Hd)为0.929,核苷酸多样性(Pi)为0.04424,平均核苷酸差异数(K)为19.908。 应用MEGA软件,根据 D-loop序列计算了32个单倍型之间的遗传距离为0.002—0.298,单倍型的平均遗传距离为0.070(标准误为0.01)。其中单倍型1与单倍型29、单倍型3与单倍型6、单倍型11与单倍型15、单倍型3与单倍型20的遗传距离最小,均为0.002;单倍型26与单倍型31的遗传距离最大,为0.298。
| 遗传多样性指数Genetic diversity indices | |
| 多态性位点数 Number of polymorphic sites,S | 171 |
| 单倍型数 Number of haplotypes,H | 32 |
| 单倍型多样度 Haplotypes diversity,Hd | 0.929 |
| 核苷酸多样性 Nucleotide diversity,Pi | 0.04424 |
| 平均核苷酸差异数 Average number of nucleotide differences,K | 19.908 |
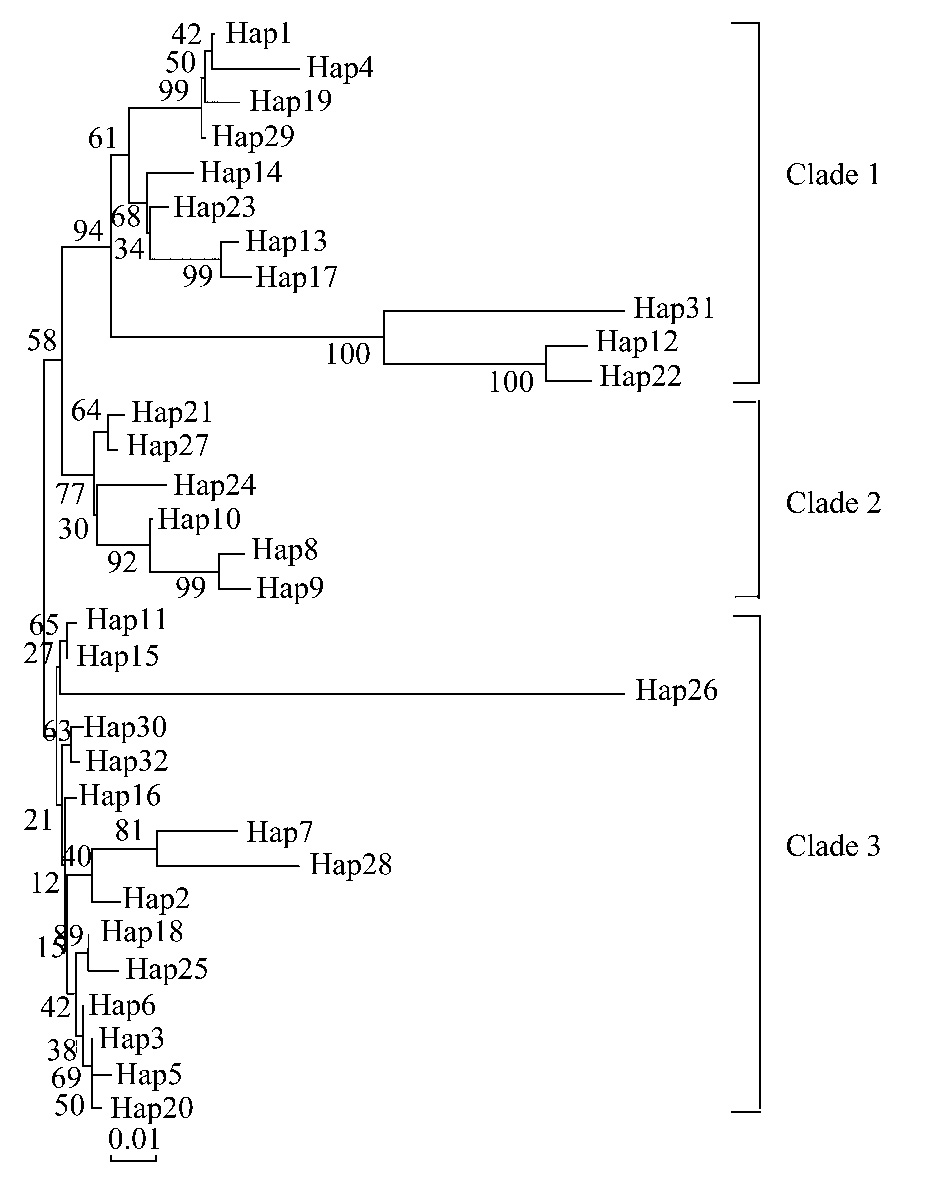
通过软件构建了陕西林麝不同群体单倍型间的NJ分子系统树(图 2),从图 2中可以看出,所有的单倍型可以被归为3个大分支,但是4个林麝群体中的单倍型是混乱分布的。分支1包含了11种单倍型,凤县野生种群有3种(Hap1、17、23)、凤县养殖场群体有2种(Hap13、14)、陇县群体有2种(Hap4、29)、留坝群体有3种(Hap1、13、19),其中Hap1是凤县野生群体和留坝群体共有的、Hap13是凤县养殖场群体和留坝群体共有的;分支2包含了6种单倍型,凤县野生群体有4种(Hap8、9、10、21)、留坝群 体有2种(Hap24、27);分支3包含了15种单倍型,凤县野生群体有10种(Hap2、3、5、6、11、15、18、20、28、32)、凤县养殖场群体有7种(Hap3、15、16、18、25、26、30)、陇县群体有2种(Hap6、7)、留坝群体有2种(Hap2、3),其中Hap2是凤县野生群体和留坝群体共有的,Hap3是凤县野生群体、凤县养殖群体和留坝群体共有的,Hap6是凤县野生群体和陇县群体共有的,Hap15、18是凤县野生群体、凤县养殖群体共有的。Network的Median-joining方法构建单倍型网络结构图显示出星状的分布态势,没有将32个单倍型区分为对应不同地理区域或者地理种群的单系群。单倍型Hap3位于星状图的中心,其他单倍型则经过1—38步突变与其相连(图 3)
|
| 图 2 陕西林麝mtDNA D-loop部分序列单倍型的Neighbour-joining分子系统树 Fig. 2 The Neighbour-joining phylogenetic tree of mtDNA D-loop haplotypes in musk deer population |
|
| 图 3 4个林麝种群D-Loop序列单倍型间的网状亲缘关系图 Fig. 3 Minimum spanning networks showed genetic relationship among haplotypes of mtDNA D-Loop gene for four forest musk deer populations |
利用 DNAsp 软件计算了陕西林麝4个不同区域mtDNA D-loop 序列的遗传多样性指数(表 3)。凤县地区野生林麝单倍型多样度(Hd)0.980;单倍型数(h)29个;核苷酸多样度(Pi)0.03594;多样性位点142 个。凤县养殖场林麝单倍型多样度(Hd)0.978;单倍型数(h)12个;核苷酸多样度(Pi)0.04917;多样性位点154个。留坝地区林麝单倍型多样度(Hd)0.833;单倍型数(h)6个;核苷酸多样度(Pi)0.03025;多样性位点47个。陇县地区林麝单倍型多样度(Hd)0.905;单倍型数(h)5个;核苷酸多样度(Pi)0.03962;多样性位点60个。 用Kimura 2-parameter模型计算种群内及种群间的遗传距离(表 4),4个群体的平均遗传距离为0.043(标准误SE为0.005),凤县养殖场群体与留坝群体和陇县群体的遗传距离较远,凤县野生群体和陇县群体的遗传距离较近。种群间的遗传距离反映了群体间亲缘关系的远近,由此可知,凤县养殖场群体与留坝和陇县群体的亲缘关系较远。衡量各群体间的遗传分化指标见表 5。
| 采集地 Collection sites | 样本个数(个) Number of samples | 单倍型变异度(Hd)Hyplotype diversity | 变异位点数Number of var iability locus | 单倍型数(h)Number of hyplotype | 平均核苷酸差异(K)Average number of nucleotide differences | 核苷酸多样度(Pi)Nucleotide diversity | Tajima′s D |
| 凤县野生 | 39 | 0.980 | 142 | 29 | 20.416 | 0.03594 | -1.45277(P>0.10) |
| 凤县养殖场 | 14 | 0.978 | 154 | 12 | 30.286 | 0.04917 | -1.68146(0.10>P>0.05) |
| 留坝 | 9 | 0.833 | 47 | 6 | 17.333 | 0.03025 | 0.01186(P>0.10) |
| 陇县 | 7 | 0.905 | 60 | 5 | 23.571 | 0.03962 | -0.21753(P>0.10) |
| 群体Population | 留坝 | 陇县 | 凤县(野生) | 凤县(养殖场) |
| 留坝 | 0.038(0.006) | (0.006) | (0.007) | (0.007) |
| 陇县 | 0.045 | 0.041(0.006) | (0.005) | (0.005) |
| 凤县(野生) | 0.052 | 0.042 | 0.038(0.004) | (0.004) |
| 凤县(养殖场) | 0.059 | 0.051 | 0.046 | 0.055(0.005) |
| 种群1 Pop1 | 种群2 Pop2 | 基因多样度(Hs) Gene diversity | 平均核苷酸差异数(Kxy) The average number of nucleotide differences | 基因分化系数(Gst) Gene differentiation coefficient | 遗传分化指数(Fst) Diversity coefficient | 核苷酸分歧度(Dxy) Nucleotide divergence | 核苷酸净遗传距离(Da) Net nucleotide divergence |
| 陇县 | 留坝 | 0.86310 | 19.14286 | 0.07023 | 0.11381 | 0.04254 | 0.00484 |
| 陇县 | 凤县(野生) | 0.89712 | 17.81685 | 0.03510 | 0.05563 | 0.03959 | 0.00220 |
| 陇县 | 凤县(养殖场) | 0.92545 | 21.40816 | 0.04279 | 0.05286 | 0.04757 | 0.00251 |
| 留坝 | 凤县(野生) | 0.88610 | 21.84615 | 0.03968 | 0.26632 | 0.04855 | 0.01293 |
| 留坝 | 凤县(养殖场) | 0.89695 | 24.65873 | 0.04505 | 0.21006 | 0.05480 | 0.01151 |
| 凤县(野生) | 凤县(养殖场) | 0.90539 | 19.19231 | 0.00643 | 0.00712 | 0.04265 | 0.00033 |
本研究通过测序分析得出秦岭地区林麝4个群体mtDAN D-Loop区的变异位点为171个,占分析位点的27.05%,变异程度比同一地区林麝种群的Cytb基因片段中检测到37个变异位点(约占8.68%)的结果高[26],这再次证明了D-loop的进化速率比mtDNA其它区域快。
同时结果显示,林麝的G含量比其他3个碱基含量低,显示较明显的碱基偏倚,这是由于蛋白质编码基因的核苷酸突变在密码子第三位点上受到的自然选择压力较小所致,证明密码子第三位点能够更清晰地表明线粒体基因组核苷酸组成的不均一性[27, 28]。
3.2 林麝人工养殖对林麝遗传多样性的影响长期以来,我国对麝香的年需求量非常大,接近2000kg[29],而野生麝资源持续下降,从20世纪50年代起,为了解决麝香短缺问题,我国许多地方开始人工养麝,陕西省凤县是国内养殖数量最大的地区[30]。本研究中,林麝养殖场群体的Tajima′s D值为-1.68146(表 3),其显著性高于其他3个群体,0.10>P>0.05,说明养殖场群体的林麝有种群扩张和定向选择的趋势,其他3个野生群体的Tajima′s D值不显著背离0,复合中性突变[31]。而且养殖场群体的单倍型变异度(Hd)仅低于凤县野生群体,核苷酸多样度(Pi)为4个群体中最高,说明虽然人工养殖条件下,并没有出明显的现近繁殖导致的遗传多样性降低的情况。这与当地养殖户会从四川、上海等地引进林麝,并对每头林麝进行身份标记,防止近亲繁殖有关。四川省林麝养殖已有50多年历史[17],陕西省所有规模较大的养殖户都有从四川各个养殖场引进林麝的记录。有近10户养殖户及凤县养殖场有从上海林麝养殖场引进林麝的记录。同时,从4个群体间的遗传距离来看(表 4),凤县养殖场群体和凤县野生群体的遗传距离小于和其他两个群体的遗传距离。这与当地养殖户会收养凤县地区生病野生林麝并进行繁殖有关。由此来看,虽然近几年凤县地区林麝养殖发展迅速,但是由于定期引进外地林麝并防止近亲繁殖的工作到位,人工养殖麝群并没有出现遗传多样性降低的情况。所以在养殖户出现的初生麝畸形、雄性死亡率偏高的情况[32]遗传多样性高低关系不大。
3.3 陕西林麝群体的遗传多样性遗传多样性是估计种群长期生存可能性重要指标,也是生物学上制定保护计划所必需的内容之一。遗传多样性的丧失会引起个体繁殖适合度的下降。应用mtDNA测序技术来研究物种的遗传多样性时,通常用几个重要指标来衡量一个群体mtDNA的遗传变异程度,单倍型间的平均遗传距离(P)、核苷酸多样性(Pi)和单倍型多样度值(Hd)[33, 34]。一般大多数哺乳动物的P值都在0.01以上,就被认为变异大[35]。本实验结果显示,4个群体单倍型间的平均遗传距离为0.043,大于0.01,这说明陕西林麝群体的遗传变异较大。Hd值是单倍型多样度,指样本中随机抽取到两个不同单倍型的频率;Pi值是核苷酸多样度,指序列间每个位点的平均核苷酸差异数。Hd值和Pi值越大,群体的多态程度越高,遗传多样性越丰富[36]。根据Nei等[37]的定义,给定群体内两随机选取的mtDNA序列间Pi值越小,表明群体的遗传多样性越低。Pi值考虑了各种mtDNA单倍型在群体中比例,故在反映一个群体mtDNA的多态程度时比单纯的平均遗传距离更可靠。Lan等[35]认为,当Pi值在0.0015—0.0047时,群体的遗传多样性较低。本研究中,林麝4个群体mtDNA D-Loop区的核苷酸多样性(Pi)为0.04424,凤县养殖场群体核苷酸多样性最大为0.04917,留坝群体的核苷酸多样性最小为 0.03025,凤县野生群体和陇县群体居中,均大于 0.0047。与其他鹿科动物 D-Loop区部分序列的核苷酸多样性相比,大于原麝(Moschus moschiferus)0.0265[38]、梅花鹿(Cervus nippon)0.0106[39]、黑麂(Muntiacus muntja)0.00562[40]、海南坡鹿(Cervus eldi)0.0014—0.0024[41]。综上可知,目前陕西林麝群体遗传多样性较丰富,且凤县养殖场群体的遗传多样性丰富度最大。
从表 5各群体的遗传分化指数FST可知,凤县野生群体和凤县养殖场群体的Fst值最小为0.00712,凤县野生群体与留坝群体的Fst值最高为0.26632。可见凤县野生群体和凤县养殖场群体两者遗传分化较小,存在着较高的基因流水平,这与凤县养殖户长期收留生病或走失野生林麝有关。同时,根据Shaklee等[42]发表的资料,提出鱼类在属、种和种群三级水平上的遗传距离P值分别为0.90,0.30及0.05的分类判据。本实验结果显示,单倍型间的平均遗传距离为0.043,可见其遗传分化尚未达到种群分化的水平。
| [1] | Sheng H L. The Deer in China. East China Normal University Press, Shanghai, 1992. |
| [2] | Wang Y, Jiang H R, Xue W J. Advances in Research of Forest Musk Deer (Moschus berezovskii). Sichuan Journal of Zoology, 2006, 25(1): 195-200. |
| [3] | Zou F D, Yue B S, Xu L, Zhang Y Z. Isolation and characterization of microsatellite loci from forest musk deer. Zoological Science, 2005, 22(5): 593-598.. |
| [4] | Sheng H L. The Current status of Chinese musk deer resources and saving countermeasures. Chinese of Wildlife, 1996, 91(3): 10-12. |
| [5] | Le P Q, Chen Y Y. China Red Data Book of Endangered Animals. Science Press, Beijing, 1998. |
| [6] | Yang Q S, Meng X X, Xia L, Feng Z J. Conservation status and causes of decline of musk deer (Moschus spp.) in China. Biological Conservation, 2003, 109(3): 333-342.. |
| [7] | Meng X X, Zhou C Q, Hu J C, Li C, Meng Z B, Feng J C, Zhou Y J, Zhu Y J. Musk deer farming in China. Animal Science, 2006, 82(1): 1-6. |
| [8] | Sheng H L; Liu Z X. The Musk Deer in China.Shanghai Science and Technology Press, Shanghai, 2007. |
| [9] | Jiang Y A. Number estimate of Musk deer (Muschus berezovskii) of Shaanxi province. Journal of Shaanxi Normal University(Natural Science Edition), 1997, 25: 127-130. |
| [10] | Liu W H, Yue N Y, Zhang H F. Present situation and analysis of Shaanxi domestic musk deer resources. Journal of Shaanxi Normal University (Natural Science Edition), 2006, 34(3): 183-187. |
| [11] | Wu J Y, Wang W. The Musk Deer of China. China Forestry Publishing House, Beijing, 2006. |
| [12] | Zhou J L, Zhang Y P, Huang M H. Phylogenetic Relationships Among Crotalinae Based on Mitochondrial Cytochrome B Gene Sequence Variations. Current Zoology, 2001, 47: 361-366. |
| [13] | Sun W L, Yang B H, Cao X L. Phylogenetic Relationship and Genetic Diversity of Chinese four domestic donkeys using mtDNA D-Loop. China Herbivores, 2007, 27(2): 7-10. |
| [14] | Hiendleder S, Mainz K, Plante Y, Lewalski H. Analysis of mitochondrial DNA indicates that domestic sheep are derived from two different ancestral maternal sources: no evidence for contributions from urial and argali sheep. Journal of Heredity, 1998, 89(2): 113-120. |
| [15] | Zhang T, Lu H C. Genetic Diversity of Mitochondrial DNA D-loop Sequences in Ningqiang Pony. Scientia Agricultura Sinica, 2012, 45(8): 1587-1594. |
| [16] | Peng H Y, Zhang X Y, Yue B X. A Primary Analysis on the Amplification of the Complete Mitochondrial Genome of Forest Musk Deer (Moschus Berezovskii) and Their Sequence Structures. Journal of Yulin Teachers College, 2011, 32(2): 63-68. |
| [17] | Peng H, Liu S, Zou F, Zeng B, Yue B. Genetic diversity of captive forest musk deer (Moschus berezovskii) inferred from the mitochondrial DNA control region. Animal Genetics, 2009, 40(1): 65-72. |
| [18] | Zhou YQ, Zhu W, Liu Z P, Wu WQ. A Quick Method of Extraction of DNA by Chelex-100 from Trace Bloodstains. Fudan University Journal of Medical Sciences, 2003, 30: 379-380. |
| [19] | Joe Sambrook, David W Russell. Molecular Cloning. A Laboratory Manua, 3rd ed. Cold Spring Harbor Laboratory Press, 2001, 463-470. |
| [20] | Sambrook J, Russell D W. Molecular Cloning: A Laboratory Manual. 3rd ed. New York: Cold Spring Harbor Laboratory Press, 2001: 463-470. |
| [21] | Yue G H, Li Y, Lim L C, Lim L C, Orban L. Monitoring the genetic diversity of three Asian arowana (Scleropages formosus) captive stocks using AFLP and microsatellites. Aquaculture, 2004, 237(1/4): 89-102. |
| [22] | Galtier N, Gouy M, Gautier C. SEAVIEW and PHY LO-WIN: two graphic tools for sequence alignment and molecular phylogeny. Computer Applications Bioscience, 1996, 12(6): 543-548. |
| [23] | Rozas J, Sánchez-DelBarrio J C, Messeguer X, Rozas R. DnaSP, DNA polymorphism analyses by the coalescent and other methods. Bioinformatics, 2003, 19(18): 2496-2497. |
| [24] | Tamura K, Peterson D, Peterson N, Nei M, Kumar S. MEGA5: molecular evolutionary genetics analysis using maximum likelihood, evolutionary distance, and maximum parsimony methods. Molecular Biology and Evolution, 2011, 28(10): 2731-2739. |
| [25] | Bandelt H J, Forster P, Rohl A. Median-joining networks for inferring intraspecific phylogenies. Molecular Biology and Evolution, 1999, 16(1): 37-38. |
| [26] | Feng H, Feng C L. Hair DNA Extraction and Phylogenic Analysis of Forest Musk Deer (Moschus berezovskii). Acta Agriculturae Borealioccidentalis Sinica, 2012, 21(8): 14-18. |
| [27] | Meyer A. Evolution of Mitochondrial DNA in Fishes. Amsterdam: Elsevier Press, 1993: 1-36. |
| [28] | Li A. Gao T X, Sun D R. Comparative Analysis of White Croaker (Pennahia argentata) Based on Complete Cytochrome b Gene Sequence in Mitochondrial DNA. Journal of Fishery Sciences of China, 2010, 16: 1166-1171. |
| [29] | Zhong L B, Wu Y Q. The Breeding and Protection of musk deer in china. TRAFFIC East Asia, HongKong, 2001, 11-33. |
| [30] | Su L N, Hou Q K, Che LF. Prospect on the Musk Deer Farming in Shaanxi Province. Shaanxi Journal of Agricultural Sciences, 2011, 57: 159-161. |
| [31] | Guo Y B. Genetic Diversity, Origin and Genetic Differentiation of Ten Sheep Breeds Using Mitochondrial DNA D-loop Region. Shandong Agricultural University, Shandong, 2010. |
| [32] | Hu Z J, Wang Y, Xue W J. Domestic Rearing of Forest Musk Deer (Moschus berezovskii) in Fengxian County, Shaanxi, China: History, Status and Reproductive Characteristics. Sichuan Journal of Zoology, 2007, 26: 948-951. |
| [33] | Nei J E, Avise J C. Application of a random walkmodel to geographic distributions of animal mitochondrial DNA variation. Genetics, 1993, 135(4): 1209-1220. |
| [34] | Peng S, Dai Y G. Sequence Polymorphism of mtDNA D-Loop in the Population of the Endangered Species Onychostoma Rara From the Qingshui River. Journal of Fisheries of China, 2009, 33: 196-200. |
| [35] | Lan H, Shi L M. The origin and genetic differentiation of native breeds of pigs in southwest China: An approach from mitochondrial DNA polymorphism. Biochemical Genetics, 1993, 31(1/2): 51-60. |
| [36] | Zhang L, Gun S B. Analysis of Genetic Diversity and Phylogeny of Five Chinese Subspecies of Wapiti Using Mitochondrial Cytb Complete Sequence. Acta Agriculturae Boreali-Sinica, 2010, 25(4): 12-16. |
| [37] | Nei J E, Avise J C.Application of random walkmodel to geographic distributions of animal mitochondrial DNA variation.Genetics, 1993, 135(4):1209-1220. |
| [38] | Ma X Z. Genetic Diversity and Preservation Measures for Germplasm Resources of Musk Deer in China Northeast Forestry University, Hei Longjiang, 2012. |
| [39] | Wu H, Wang Q H, Fang S G. Two genetically distinct units of the Chinese sika deer (Cervus nippon): analyses of mitochondrial DNA variation. Biological Conservation, 2004, 119(2): 183-190. |
| [40] | Wu H L, Fang S G. Mitochondrial DNA genetic diversity of black muntjac (Muntiacus crinifrons): an endangered species endemic to China. Biochemical Genetics, 2005, 43(7/8): 407-416. |
| [41] | Balakrishnan C N, Monfort S L, Gaur A, Singh L, Sorenson M D. Phylogeography and conservation genetics of Elds deer (Cervus eldi). Molecular Ecology, 2003, 12(1): 1-10. |
| [42] | Shaklee J B, Tamaru C S, Waples R S. Speciation and evolution of marine fishes studied by the electrophoretic analysis of proteins. Pacific Science, 1982, 36(2): 141-157. |
| [1] | 盛和林. 中国鹿类动物. 上海: 华东师范大学出版社, 1992. |
| [2] | 王淯, 姜海瑞, 薛文杰. 林麝 (Moschus berezovskii) 研究概况和进展. 四川动物, 2006, 25(1): 195-200. |
| [4] | 盛和林. 我国麝资源现状及救护措施. 野生动物, 1996, 91(3): 10-12. |
| [5] | 国家林业局办公室. 国家林业局令(第七号). 2003. 2. 24. |
| [8] | 盛和林, 刘志霄. 中国麝科动物. 上海: 上海科技技术出版社, 2007. |
| [9] | 江廷安. 陕西省林麝的数量估计. 陕西师范大学学报: 自然科学版, 1997, 25(增刊): 127-130. |
| [10] | 刘文华, 岳乃鱼, 张洪峰. 陕西省家养林麝资源现状与分析研究. 陕西师范大学学报: 自然科学版, 2006, 34(3): 183-187. |
| [11] | 吴家炎, 王伟. 中国麝类. 北京: 中国林业出版社, 2006. |
| [12] | 周继亮, 张亚平, 黄美华, 陈永久, 陈小青, 姚耿东. 蝮亚科蛇线粒体细胞色素b基因序列分析及其系统发育. 动物学报, 2001, 47(4): 361-366. |
| [13] | 孙伟丽, 杨博辉, 曹学亮, 孙永峰, 梁春年, 刘建斌. 中国四个地方驴品种mtDNA D-Loop部分序列分析与系统进化研究. 中国草食动物, 2007, 27(2): 7-10. |
| [15] | 张涛, 路宏朝. 宁强矮马线粒体DNA D-loop区的遗传多样性. 中国农业科学, 2012, 45(8): 1587-1594. |
| [16] | 彭红元, 张修月, 岳碧松. 林麝线粒体基因组扩增及其序列结构的初步分析. 玉林师范学院学报, 2011, 32(2): 63-68. |
| [18] | 周月琴, 朱伟, 刘志萍, 吴文庆. 用Chelex-100快速提取微量血痕中的DNA. 复旦学报: 医学版, 2003, 30(4): 379-380. |
| [19] | 蔡振媛, 张同作, 连新明, 慈海鑫, 苏建平. 一种提取动物基因组总DNA的野外样品保存方法. 四川动物, 2006, 25(3): 473-477. |
| [26] | 冯慧, 冯成利, 刘晓农, 任轶. 陕西省林麝毛发DNA的提取及系统发育分析. 西北农业学报, 2012, 21(8): 14-18. |
| [28] | 李昂, 高天翔, 孙典荣. 中国近海与日本近海白姑鱼线粒体细胞色素b基因全序列比较分析. 中国水产科学, 2010, 17(6): 1166-1171. |
| [29] | 钟乐邦, 吴郁琪. 中国的养麝场与麝的保护工作. 香港: 东亚野生物贸易研究委员会, 2001: 11-33. |
| [30] | 苏丽娜, 侯罄康, 车利锋, 唐婕, 吴晓民. 陕西省人工养麝业展望. 陕西农业科学, 2011, 57(2): 159-161. |
| [31] | 郭彦斌. 利用mtDNA D-loop区研究10个绵羊品种的遗传多样性、起源及遗传分化 [D]. 济南: 山东农业大学, 2010. |
| [32] | 胡忠军, 王淯, 薛文杰, 姜海瑞, 徐宏发. 陕西凤县林麝家庭养殖: 历史、现状与繁殖特性. 四川动物, 2007, 26(4): 948-951. |
| [34] | 彭珊, 代应贵. 濒危鱼类稀有白甲鱼清水江种群mtDNA D-loop序列多态性. 水产学报, 2009, 33(2): 196-200. |
| [36] | 张丽, 滚双宝, 雷天云, 刘丽霞, 秦大伟, 赵世峰. 应用mtDNA Cytb基因全序列分析中国5个马鹿群体的遗传多样性和系统发育. 华北农学报, 2010, 25(4): 12-16. |
| [38] | 马晓哲. 我国原麝遗传多样性研究及其种质资源保存对策探讨 [D]. 哈尔滨: 东北林业大学, 2012. |
 2013, Vol. 34
2013, Vol. 34