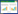文章信息
- 曾志华, 杨民和, 佘晨兴, 仝川
- ZENG Zhihua, YANG Minhe, SHE Chenxing, TONG Chuan
- 闽江河口区淡水和半咸水潮汐沼泽湿地土壤产甲烷菌多样性
- Diversity of methanogen communities in tidal freshwater and brackish marsh soil in the Min River estuary
- 生态学报, 2014, 34(10): 2674-2681
- Acta Ecologica Sinica, 2014, 34(10): 2674-2681
- http://dx.doi.org/10.5846/stxb201307191916
-
文章历史
- 收稿日期:2013-7-19
- 网络出版日期:2014-2-20
2. 福建师范大学环境科学与工程学院, 福州 350007;
3. 湿润亚热带生态-地理过程教育部重点实验室, 福州 350007;
4. 福建师范大学亚热带湿地研究中心, 福州 350007
2. College of Environmental Science and Engineering, Fujian Normal University, Fuzhou 350007, China;
3. Key Laboratory of Humid Subtropical Eco-geographical Process of Ministry of Education, Fuzhou 350007, China;
4. Research Centre of Wetlands in Subtropical Region, Fujian Normal University, Fuzhou 350007, China
入海河口位于河流与海洋交汇处,河口区从上游段到下游段,根据盐度的不同,依次分布有潮汐淡水、潮汐半咸水(或微咸水)沼泽湿地以及潮汐咸水湿地(包括盐沼和红树林)[1]。潮汐沼泽湿地是全球天然湿地重要的组成部分,也是世界上初级生产力最高的植物群落类型之一。具有高热辐射吸收潜力的甲烷被认为是重要的温室气体之一[2],据估算天然湿地甲烷排放占全球甲烷排放总量的21%以上[3]。产甲烷菌是介导湿地土壤甲烷产生的功能菌群,对于不同湿地类型的土壤产甲烷菌群落结构的测定有助于正确认识湿地甲烷代谢的微生物学机制。
随着分子生物学技术在湿地土壤微生物种类与数量的测定方面的广泛应用,北方泥炭湿地等湿地类型土壤产甲烷菌群落结构的研究报道较多[4, 5, 6, 7],近年来,关于河口潮汐淡水沼泽[8]和河口咸水沼泽湿地[9, 10]土壤产甲烷菌群落结构的研究日益增多。盐度是入海河口区一个十分重要的环境因子,盐度变化对于河口潮汐沼泽湿地植物群落特征具有直接的影响[11, 12]。盐度变化对于河口潮汐沼泽湿地甲烷代谢的影响也已引起科学家的关注[13, 14, 15, 16]。Baldwin等[17]采用微型实验生态系的方法,向淡水湿地土芯添加不同盐度的NaCl溶液,同时通过末端标记限制性片段长度多态性分析(T-RFLP)测定,结果表明随着盐度的增加,土壤产甲烷菌群落结构发生变化,一些产甲烷菌种消失。然而,目前还未见关于河口区从淡水到半咸水盐度梯度上分布的同一优势沼泽植物群落湿地土壤产甲烷菌群落结构变化的报道。本研究以闽江河口区为研究范围,运用PCR-RFLP技术和测序相结合的方法,测定和分析了从淡水到半咸水盐度梯度上分布的4个短叶茳芏潮汐沼泽湿地土壤产甲烷菌的群落结构和系统发育,研究结果为更深入地认识盐度变化对于河口区沼泽湿地土壤产甲烷菌多样性的影响提供了基础数据。
1 材料与方法 1.1 研究区和样地概况闽江河口区气候暖热湿润,年均降水日数153 d,年均降水量1346 mm,降水多发生在3—9月。闽江河口区潮汐特征表现为口外正规半日潮,口内非正规半日浅海潮[18]。闽江河口区从河口海滨段向上至中游段依次分布有鳝鱼滩湿地、蝙蝠洲湿地、下洋洲湿地和塔礁洲湿地(图1),其中下洋洲和塔礁洲为典型的淡水潮汐湿地,鳝鱼滩和蝙蝠洲受海水影响较大,近岸沼泽植被带属于半盐水沼泽湿地,4个湿地上均分布有短叶茳芏(Cyperus malaccensis Lam. var. brevifolius Bocklr.)群落。短叶茳芏为多年生草本植物,耐盐碱性强,广泛分布于我国的闽、粤等沿海省份和台湾地区。4个湿地分布的短叶茳芏沼泽群落结构简单,多为单一种群落,短叶茳芏植株3月初进入生长期,6—9月生长旺盛,花期较短,7月份植株高度1.5—2 m。
|
| 图 1 4个研究样地在闽江河口区的分布 Fig. 1 Spatial distribution of four sampling tidal marshes in the Min River estuary |
2012年6月29—30日,在4个湿地分别选择1个长势均匀的短叶茳芏群落为研究样地,在鳝鱼滩湿地,短叶茳芏群落集中分布于近堤岸的中高潮滩,在其他3个湿地短叶茳芏群落均分布在近河岸一侧。在与河岸线或海岸线平行的方向随机布设3个样点(样点间约3—5 m间距),用不锈钢采样器采集表层(0—10 cm)土样,采样均在落潮后时段进行,样品采集后迅速装入灭菌的封口聚乙烯袋中,并置于冰盒中尽快送至实验室,进行DNA提取和后续分析。
1.3 土壤理化指标的测定土壤pH值原位采用IQ150便携式pH/氧化还原电位/温度计(IQ Scientific Instruments,USA)测定,土壤电导率原位用2265FS便携式电导计(Spectrum Technologies Inc.,USA)测定,并以此表征土壤盐度[19]。土壤含水量和容重采用环刀采样,105 ℃烘干直至恒重并测定。土壤质地采用激光粒度仪(Mastersizer-2000,UK)测量。土壤有机碳(SOC)采用重铬酸钾氧化法测定。
1.4 土壤总DNA的提取0.25 g土样总DNA的提取使用Power Soil DNA isolation kit (MO BIO Laboratories,USA),按照厂家说明书的方法对土样DNA的提取,并以1%浓度的琼脂糖凝胶电泳检测、分析。提取好的DNA存于-20 ℃贮存备用。
1.5 mcrA基因的PCR扩增和纯化以土壤总DNA为模板,利用产甲烷菌的特异性引物ME1(GCMATGCARATHGGWATGTC)和ME2(TCATKGCRTAGTTDGGRTAGT) [20]进行扩增。扩增反应体系(50 μL):10× buffer缓冲液5 μL,dNTP 4 μL,引物ME1 1 μL,引物ME2 1 μL,DNA模板2 μL,Taq酶0.5 μL,加无菌去离子水至50 μL。
PCR反应程序:95 ℃预变性5 min; 94 ℃变性45 s,50 ℃退火45 s,72 ℃延伸90 s,33个循环;最后72 ℃延伸10 min。PCR产物用1%的琼脂糖凝胶电泳检测。在紫外灯下将扩增出的条带切下,用SanPrep柱式DNA胶回收试剂盒(sanggon),按照说明书进行mcrA基因回收。
1.6 mcrA基因的T-A克隆及克隆文库的构建回收后的mcrA基因与PMD18-TVector(TaKaRa) 根据载体说明书进行连接:连接体系(10 μL):PMD18-TVector 1 μL,PCR产物 3 μL,灭菌的ddH2O 1 μL,SolutionⅠ 5 μL,将上述体系配好后轻轻混匀,16 ℃反应3 h。连接结束后,将连接液转入E.coli DH5α感受态细胞,转化产物涂布到含有氨苄青霉素的LB固体培养基上,37 ℃培养12—16 h。采用蓝白斑筛选挑取适量的阳性克隆构建克隆文库。在构建的文库中挑取100个阳性克隆进行菌落PCR的随机验证,根据扩增条带的大小鉴定重组子。
1.7 mcrA基因克隆文库的RFLP分析,测序和系统发育分析选择含有正确插入片段的阳性克隆并对其PCR产物进行酶切。酶切体系:菌落PCR产物5 μL,0.1%BSA 1 μL,10×T Buffer 1 μL,限制性内切酶MSPⅠ0.5 μL,加灭菌去离子水补充至10 μL,37 ℃反应3 h。酶切后产物用2.0%的琼脂糖凝胶电泳分离酶切片段,比较分析酶切电泳图谱,将酶切谱型完全一致的归为1个操作分类单位(operational taxonomic unit,OTU),将不同的酶切谱型所对应的克隆子送上海英俊公司(Invitrogen)测序。得到序列与GeneBank数据库中已有的序列进行Blast比对,找到亲缘关系最近的种属,确定其分类地位。所有序列用Cluster X Version 1.83软件进行序列比对分析,利用MEGA4软件,采用NJ法,自展数1000,建立系统发育树。
1.8 多样性分析根据酶切图谱信息,计算克隆文库的库容C,计算公式[21]如下:
C=[1-(n1/N)]×100%
式中,n1代表文库中仅出现1次的OTU数目,N代表每个文库中的总阳性克隆数。利用Bio-dap软件对Shannon-Weaver指数(H)和Simpson指数(D)进行计算。
2 结果与分析 2.1 土壤理化特征鳝鱼滩短叶茳芏样地土壤盐度显著高于下洋洲和塔礁洲的短叶茳芏样地。4个短叶茳芏样地土壤容重及DOC含量均无显著性差异。鳝鱼滩短叶茳芏样地土壤pH值显著高于其它3个样地,而SOC含量显著小于其它3个样地。4个样地土壤以粉粒为主,随着盐度的降低,短叶茳芏湿地土壤粉粒逐渐减少,而砂粒含量不断增加(表1)。
| 理化性质 Physicochemical property | 鳝鱼滩 Shanyutan | 蝙蝠洲 Bianfuzhou | 下洋洲 Xiayangzhou | 塔礁洲 Tajiaozhou |
| 数据为平均值±标准误,同一行数据标注不同字母表示差异性显著,P < 0.05,n = 3 | ||||
| NaCl溶液电导率/(mS/cm) | 1.97±0.54 a | 1.29±0.39 ab | 0.42±0.03 b | 0.46±0.01 b |
| pH | 6.68±0.03 a | 5.58±0.06 b | 4.51±0.03 b | 5.87±0.06 c |
| 容重Bulk density/(g/cm) | 0.74±0.07a | 0.78±0.04 a | 0.78±0.01 a | 0.66±0.03 a |
| SOCSoil organic carbon/ (g/kg) | 25.80±0.3c | 53.40±4.1a | 37.20±1.9b | 51.70±4.5a |
| 粘粒Cosmid /% | 13.40±1.80 ab | 15.00±0.45 a | 12.30±0.08 a | 10.60±0.24 b |
| 粉粒Silt /% | 70.20±1.86 a | 67.00±0.57 a | 63.00±0.63 b | 49.40±0.74c |
| 砂粒Sand/% | 16.40±3.06 c | 18.00±1.00 c | 24.70±0.70b | 40.00±0.70 a |
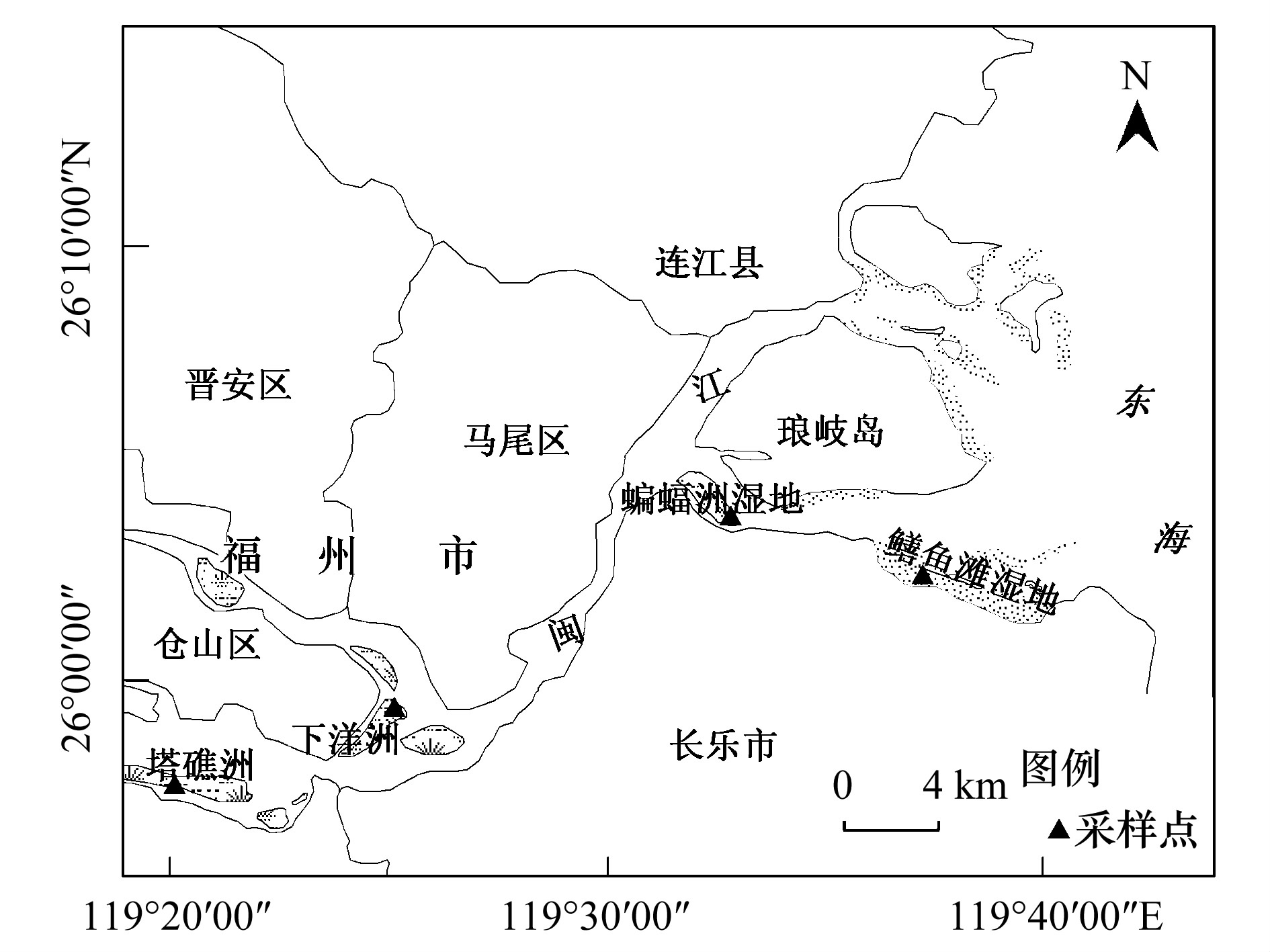
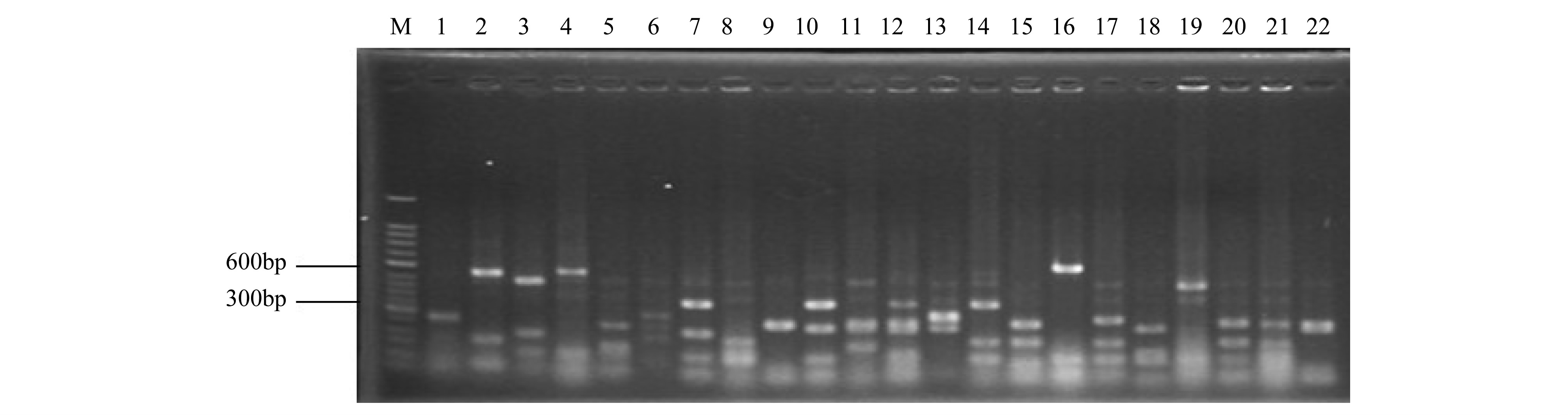
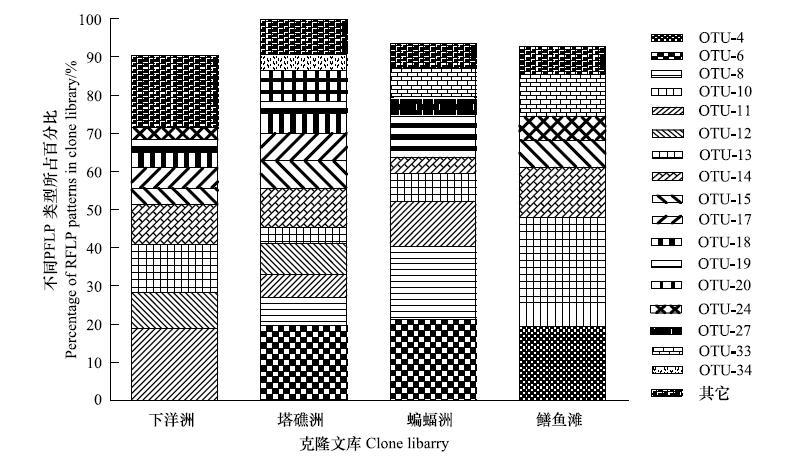
通过RFLP方法,对下洋州、塔礁洲、蝙蝠洲和鳝鱼滩短叶茳芏沼泽湿地土壤分别获得的95、97、94和98个含有正确插入片段的阳性克隆进行单酶切分析,部分酶切图谱如图2所示。从所有酶切图谱看,不同文库间有一些相似的酶切类型,表现在酶切条带与Marker的相对位置上,这表明不同盐度短叶茳芏湿地土壤中可能有一定比例的共有类群,这些类群不受盐度变化的影响。4个样点克隆文库分别获得26、21、16和16种不同的RFLP带型,克隆文库RFLP分析见表2。从RFLP分析结果来看,半咸水的蝙蝠洲和鳝渔滩短叶茳芏沼泽湿地土壤的2个克隆文库相似,均与淡水的下洋洲和塔礁洲短叶茳芏沼泽湿地土壤存在很大的区别。从表2可以看出4个样点产甲烷菌克隆文库的覆盖率均较高,分别为93.6%、93.8%、89.4%和91.0%,可以说建立的文库已覆盖研究样地土壤产甲烷类群的90%以上。塔礁洲和鳝鱼滩短叶茳芏沼泽湿地土壤克隆文库种类(部分未列出)较为丰富,在所有文库中,OTU-11、OTU-6、OTU-13和OTU-14是主要的优势群,占整个RFLP类型的34.90%(图3)。OTU-14存在于4个样地中,但在塔礁洲短叶茳芏沼泽样地中所占比例最高。蝙蝠洲和鳝鱼滩短叶茳芏沼泽土壤克隆文库主要的酶切类型是OTU-6、OTU-8、OTU-13和OTU-4,下洋洲和塔礁洲短叶茳芏沼泽土壤克隆文库主要的谱型是OTU-11、OTU-14和OTU-16。
4个短叶茳芏沼泽湿地土壤产甲烷菌的Simpson指数值和Shannon-Wiener指数值如表2,下洋洲和塔礁洲淡水潮汐沼泽湿地土壤产甲烷菌多样性指数Shannon-Wiener分别为2.81和2.65,蝙蝠洲和鳝鱼滩半咸水潮汐沼泽湿地土壤Shannon-Wiener多样性指数分别为2.33和2.27,2个淡水沼泽多样性指数差别不大且均高于半咸水沼泽,Simpson指数分析结果也与之类似。结果表明淡水潮汐沼泽湿地土壤产甲烷菌多样性高于半咸水潮汐沼泽湿地。
|
| 图 2 mcrA基因插入片段的MspⅠ酶切图谱(部分) Fig. 2 Insert of mcrA genes digested by MspⅠ(partial) |
|
| 图 3 mcrA基因克隆文库酶切类型百分比 Fig. 3 Percentage of RFLP patterns of mcrA gene clone library |
| 克隆文库 Clone library | 单一酶切克隆数 Number of single phylotype | 酶切类型数 Total number of phylotype | 阳性克隆数 Number of positive clones | 香农-威纳指数 Shannon-Weiner index | 辛普森指数Simpson index | 库容(C) Coverage(C)/% |
| 鳝鱼滩Shanyutan | 6 | 16 | 98 | 2.27 | 0.125 | 93.8 |
| 蝙蝠洲Bianfuzhou | 6 | 16 | 94 | 2.33 | 0.114 | 93.6 |
| 下洋洲Xiayangzhou | 10 | 26 | 95 | 2.81 | 0.076 | 89.4 |
| 塔礁洲Tajiaozhou | 9 | 21 | 97 | 2.65 | 0.081 | 91.0 |
根据酶切分类结果,每一类型的分类操作单元中选取一个单克隆菌液进行mcrA序列测定,构建的4个克隆文库中总共35个克隆子被测序。将所测序结果用Blast在GeneBank数据库中进行比对,比对结果显示,不同的RFLP类型克隆子可能代表同1个属,4个不同盐度土壤的克隆子与GeneBank数据中产甲烷菌的mcrA序列相似范围在91%—99%,并且90%以上都是不可培养的产甲烷古菌序列。将测序结果用Cluster进行序列比对,用MEGA4进行系统发育分析,结果如图4。从图4可以看出闽江河口区短叶茳芏沼泽湿地土壤存在不同的产甲烷菌类群,总体看有甲烷杆菌目(Methanobacteriales),包括Methanobacterium、Methanobrevibacter和Methanobacteriaceae;甲烷微菌目(Methanomicrobiales),主要有Methanoregula,以及甲烷八叠球菌目(Methanosarcinales),主要包括Methanosarcina和Methanococcoides。淡水潮汐沼泽湿地土壤主要有Methanoregula、Methanosarcina和Methanobacterium,半咸水潮汐沼泽湿地土壤则仅以Methanoregula为主,同样可以看出随着盐度的增加,产甲烷菌类群的生物多样性降低。
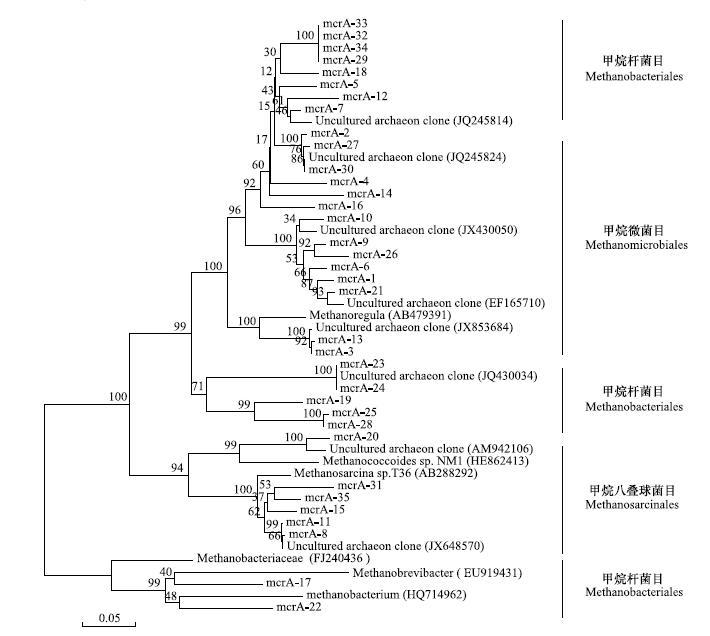
|
| 图 4 短叶茳芏湿地土壤产甲烷菌mcrA基因系统发育树 Fig. 4 Phylogenetic tree based on mcrA sequence of methanogens obtained from C. malaccensis marshes |
本研究通过PCR-RFLP技术对闽江河口区短叶茳芏沼泽湿地土壤产甲烷菌群落结构进行了分析,结果表明闽江河口区淡水-半咸水短叶茳芏潮汐沼泽湿地土壤产甲烷菌主要有3大类群:甲烷微菌目(Methanomicrobiales)、甲烷八叠球菌目(Methano-sarcinales)和甲烷杆菌目(Methanobacteriales),这与国外许多报道[4, 7, 20]一致,也与佘晨兴和仝川对闽江口鳝鱼滩芦苇潮汐沼泽湿地土壤产甲烷菌的研究结果[24]一致。但是,本研究中的淡水和半咸水短叶茳芏潮汐沼泽湿地土壤产甲烷菌群落类型有较大的差异,淡水短叶茳芏沼泽湿地土壤产甲烷菌主要类群以methanoregula、methanobacterium和 methanosarcina为主,而半咸水短叶茳芏湿地主要类群则转化为以methanoregula为主。随着盐度的增加,产甲烷菌群落多样性降低,这可能与半咸水短叶茳芏湿地产甲烷菌单一种和偶见种数减少有关。
Baldwin等[17]等研究发现,随着盐度的增加,产甲烷菌群落多样性降低,一些乙酸型产甲烷菌种类只在低盐度添加土壤中出现,而在高盐度添加土壤中未检测到,当NaCl溶液的电导率达到μS/cm时,原存在于低盐度添加土壤中的甲烷八叠球菌(methanosarcina)消失。Mishra等[25]等向洪水淹湿地中添加Cl-、SO2-4和HCO-3,结果发现产甲烷菌群落结构发生改变,其中添加Cl-的变化最显著,其次是SO2-4,而添加HCO-3,产甲烷菌群落结构无变化。Smith等[26]以mcrA基因为引物开展的自然盐田研究发现,高盐度和低盐度的土壤中产甲烷菌群落结构不一样,随着盐度的逐渐降低,甲烷微菌目成为主要的产甲烷菌类群。在本研究中,随着盐度的增加,位于蝙蝠洲和鳝鱼滩的半咸水短叶茳芏沼泽湿地土壤中甲烷八叠球菌数量减少,甲烷微菌目的methanoregula同样成为主要的产甲烷菌群。一些研究表明,钠盐、硫酸盐和硝酸盐对微生物的活动具有抑制作用,盐度越高,对微生物的抑制作用越强[27, 28, 29, 30],盐度的增大还可能影响厌氧发酵过程中电子受体的供应[31],导致产甲烷菌可利用底物发生变化从而影响产甲烷菌群落结构。在闽江河口区,与淡水潮汐沼泽相比,半咸水潮汐沼泽具有相对高的盐度,土壤中Na+、Cl-和SO2-4等离子浓度增大,从而抑制了某些产甲烷菌的活性。虽然多数研究表明盐度对湿地土壤产甲烷菌群落结构造成影响,但是,Jenifer等[32]对美国Altamaha River淡水湿地添加海水处理,采集土样实验室分析发现,细菌和古菌的群落结构均没有随着盐度的增加而发生改变。作为影响河口湿地土壤产甲烷菌群落结构的重要因素,关于盐度的影响还需更多的研究,由于海水成分的复杂性,产甲烷菌群落多样性具体与哪一种盐离子或多个盐离子有密切关系,有待进一步研究。
虽然分子生物学技术克服了产甲烷菌难培养的缺点,但是依然有一定的局限性。从酶切分析结果来看,得到的OTU数目不是很多,这可能会影响多样性的分析结果,在以后的实验中可以采用双酶切,得到更多的OTU,对产甲烷菌进行更精确的分类。PCR的偏好性可能会导致测定的产甲烷菌比实际的低,今后可通过增加取样地点、同时使用不同的引物对闽江口河口区短叶茳芏湿地土壤产甲烷菌群落结构开展更准确的研究。
| [1] | Odum W E.Comparative ecology of tidal freshwater and salt marshes.Annual Review of Ecology and Systematics,1988,147-176. |
| [2] | Segers R. Methane production and methane consumption: a review of process underlying wetland methane fluxes. Biogeochemistry, 1998, 41(1):23-51. |
| [3] | Bartlett K B, Harris R C. Review and assessment of methane emissions form wetlands. Chemosphere, 1993, 26(14):261-320. |
| [4] | Galand P E, Saarnio S, Fritze H, Yrjälä K. Depth related diversity of methanogen Archaea in Finnish oligotrophic fen. FEMS Microbiology Ecology, 2002, 42(3): 441-449. |
| [5] | Zhang G, Tian J, Jiang N, Guo X, Wang Y, Dong X. Methanogen community in Zoige wetland of Tibetan plateau and phenotypic characterization of a dominant uncultured methanogen cluster ZC-I. Environmental Microbiology, 2008, 10(7):1850-1860. |
| [6] | Freitag T E, Toet S, Ineson P, Prosser J I. Links between methane flux and transcriptional activities of methanogens and methane oxidizers in a blanket peat bog. FEMS Microbiology Ecology, 2010,73(1): 157-165. |
| [7] | Narihiro T, Hori T, Nagata O, Hoshino T, Yumoto I, Kamagata Y.The Impact of aridification and vegetation type on changes in the community structure of methane-cycling microorganisms in Japanese wetland soils.Bioscience, Biotechnology, and Biochemistry, 2011,75(9):1727-1734. |
| [8] | Morrissey E M, Berrier D J, Neubauer S C, Franklin R B. Using microbial communities and extracellular enzymes to link soil organic matter characteristics to greenhouse gas production in a tidal freshwater wetland. Biogeochemistry, 2013, doi:10.1007/s10533-013-9894-5. |
| [9] | Yuan J J, Ding W X, Liu D Y, Xiang J, Lin Y X. Methane production potential and methanogenic archaea community dynamics along the Spartina alterniflora invasion chronosequence in a coastal salt marsh. Applied Microbiology Biotechnology, 2013, doi: 10.1007/s00253-013-5104-6. |
| [10] | Zeleke J, Sheng Q, Wang J G, Huang M Y, Xia F, Wu J H, Quan Z X. Effects of Spatina alterflora invasion on the communities of methanogens and sulfate-reducing bacteria in estuarine marsh sediments. Frontiers in Microbiology, 2013, doi:10.3389/fmicb.2013.00243. |
| [11] | McKee K L,Mendelssohn I A. Response of a freshwater marsh plant community to increased salinity and increased water level.Aquatic Botany,1989,34(4):301-316. |
| [12] | Gough L,Grace J B.Effects of flooding, salinity and herbivory on coastal plant communities,Louisiana,United States.Oecologia,1998,117(4):527-535. |
| [13] | DeLaune R D,Smith C J,Patrick W H.Methane release from Gulf coast wetlands.Tellus B,1983,35B(1): 8-15. |
| [14] | Bartlett K B,Bartlett D S,Harris R C,Sebacher D I.Methane emission along a salt marsh salinity gradient.Biogeochemistry,1987,4(3):183-202. |
| [15] | Sotomayor D,Corredor J E,Morell J M.Methane flux from mangrove sediments along the southwestern coast of Puerto Rico.Estuaries,1994,17(1):140-147. |
| [16] | Poffenbarger H, JNeedelman B A, Megonigal J P.Salinity influence on methane emissions from tidal marshes.Wetlands,2011, 31(5):831-842. |
| [17] | Baldwin D S, Rees G N,Mitchell A M,Watson G,Williams J.The short-term effects of salinization on anaerobic nutrient cycle and microbial community struture in sediment from a freshwater wetland. Wetlands, 2006,26(2): 455-464. |
| [18] | Liu J Q, Zeng C S, Chen N.Wetlands Research in Min River Estuary.Beijing:Science Press,2006. |
| [19] | Tamn F Y, Wong Y S. Variations of soil nutrient and organic matter content in a subtropical mangrove ecosystem. Water, Air and Soil Pollution, 1998, 103(1/4): 245-261. |
| [20] | Hales B A, Edwands C,Ritchie D A,Hall G,Pickup R W,Saunder J R.Isolation and identification of methanogen-specific DNA from blanket bog peat by PCR amplification and sequence analysis.Applied and Environmental Microbiology,1996,62(2):668-675. |
| [21] | Hill T C J, Walsh K A, Harris J A, Moffett B F. Using ecological diversity measure with bacterial communities.FEMS Microbiology Ecology,2003,43(1):1-11. |
| [22] | Emerson D, Bellows W, Keller J K, Moyer C L, Sutton-Grier A, Megonigal J P. Anaerobic metabolism in tidal freshwater wetlands:Ⅱ. Effects of plant removal on archaeal microbial communities.Estuaries and Coasts,2013,36(3):471-481. |
| [23] | Utsumi M,Belova S E,King G M,Uchiyama H. Phylogenetic comparison of methanogen diversity in different wetland soils.The Journal of General and Applied Microbiology,2003,49(2):75-83. |
| [24] | She C X,Tong C.Vertical distribution of methanogen community structures in Phragmites australis marsh soil in the Min river estuary.Acta Ecologica Sinica, 2012,32(17):5299-5308. |
| [25] | Mishra S R, PattnaiK P, Sethunathan N, Adhya T K. Anion-mediated salinity affecting methane production in a flooded alluvial soil.Geomicrobiology Journal,2003,20(6):579-586. |
| [26] | Smith J M,Green S J,Kelley CA,Prufer-Bebout L,Bebout BM. Shifts in methanogen community structure and function associated with long-term manipulation of sulfate and salinity in a hypersaline microbial mat. Environmental Microbiology,2008,10(2):386-394. |
| [27] | Wang S Y, Tanf B, Ye L, Peng Y Z. Influence of NaCl salinity on nitrogen removal of activated sludge system. Journal of Beijing University of Technology,2008,34(6):631-635. |
| [28] | Vallcro M V G,Hulshoff Pol L W,Lettinga G,Lens P N L.Effect of NaCl on thermophilic (55℃) methane degradation in sulfate reducing granular sludge reactors. Water Research,2003, 37(10): 2269-2280. |
| [29] | Manuel C, Nicolas B, Jean P D, Rene E M. Effects of nitrogen oxides and denitrication by Pseudomonas stutzeri on acetotrophic methano nogenesis by Methanosarcina mazei. FEMS Microbiology Ecology,1998,25(3):25:271-276. |
| [30] | Li B L, Wang M M, Wei G Q, Zhang D W,Wang J P. Lateral migration and accumulation of biogenic gas in the Sanhu area, Qaidam basin. Geological Review,2003,49(1):93-100. |
| [31] | Kang Y,Wang W C,Ren J H. Review of the geochemical factors effecting biogeneic gas prodution. Bulletin of Mineralogy, Petrology and Geochemistry, 2004,23(4):350-354. |
| [32] | Edminds J W, Weston N B, Joye S B, Mou X Z, Moran M A. Microbial community response to seawater amendment in low-salinity tidal sediments. Microbial Ecology, 2009,58(3):558-568. |
| [18] | 刘剑秋,曾从盛,陈 宁.闽江河口湿地研究.北京:科学出版社,2006. |
| [24] | 佘晨兴,仝川.闽江口芦苇沼泽湿地土壤产甲烷菌群落结构的垂直分布.生态学报,2012,32(17):5299-5308. |
| [27] | 王淑莹,唐冰,叶柳,彭永臻.NaCl盐度对活性污泥系统脱氮性能的影响.北京工业大学学报,2008,34(6):631-635. |
| [30] | 李本亮,王明明,魏国齐,张道伟,王金鹏.柴达木盆地三湖地区生物气横向运聚成藏研究.地质论评,2003,49(1):93-100. |
| [31] | 康晏,王万春,任军虎.生物气生成的地球化学因素分析.矿物岩石地球化学通报,2004,23(4):350-354. |
 2014, Vol. 34
2014, Vol. 34